52 Distribuzione predittiva a posteriori
Introduzione
Nell’inferenza bayesiana non ci interessa soltanto stimare i parametri di un modello (ad esempio, la probabilità \(p\) di successo in un compito con esiti binomiali). Un obiettivo altrettanto importante è prevedere dati futuri, sulla base di ciò che abbiamo già osservato. La distribuzione predittiva a posteriori serve proprio a questo: combina
- l’incertezza sui parametri, descritta dalla distribuzione a posteriori,
- la variabilità intrinseca del processo che genera i dati futuri.
In parole semplici, la distribuzione predittiva a posteriori ci dice quali risultati futuri sono plausibili, dati i dati osservati e il modello che utilizziamo per interpretarli.
52.1 Definizione formale
Supponiamo di avere dati osservati \(y = {y_1, y_2, \ldots, y_n}\), generati da un modello che dipende da un parametro ignoto \(\theta\). Questo parametro può rappresentare, a seconda del caso, una probabilità, una media, o un coefficiente di regressione.
La conoscenza iniziale su \(\theta\) è descritta da una distribuzione a priori \(p(\theta)\). Dopo aver osservato i dati, aggiorniamo tale conoscenza attraverso la formula di Bayes, ottenendo la distribuzione a posteriori:
\[ p(\theta \mid y) = \frac{p(y \mid \theta)\, p(\theta)}{p(y)} , \]
dove:
\(p(\theta \mid y)\) è la distribuzione a posteriori: rappresenta ciò che sappiamo su \(\theta\) dopo i dati.
\(p(y \mid \theta)\) è la verosimiglianza: quanto i dati osservati sono compatibili con un certo valore di \(\theta\).
\(p(\theta)\) è la distribuzione a priori.
-
\(p(y)\) è l’evidenza, cioè la probabilità totale dei dati, calcolata come
\[ p(y) = \int p(y \mid \theta) p(\theta)\, d\theta . \]
Ora vogliamo prevedere un nuovo dato, \(\tilde{y}\). In questo caso ci serve la distribuzione predittiva a posteriori \(p(\tilde{y} \mid y)\).
52.1.1 Che cos’è \(\tilde{y}\)?
- È un dato futuro o non ancora osservato.
- Per esempio, se \(y\) rappresenta il numero di successi in una serie di lanci di moneta, \(\tilde{y}\) può rappresentare i successi in una nuova serie di lanci.
52.1.2 Che cos’è \(p(\tilde{y} \mid \theta)\)?
- È la probabilità di osservare \(\tilde{y}\) se sapessimo che il parametro del modello è proprio \(\theta\).
- Nell’esempio binomiale, corrisponde alla probabilità di ottenere \(\tilde{y}\) successi su \(n_{\text{new}}\) prove, dato che la probabilità di successo è \(\theta\).
52.1.3 Come combinare \(p(\tilde{y} \mid \theta)\) e \(p(\theta \mid y)\)
Poiché non conosciamo il vero valore di \(\theta\), consideriamo tutti i valori possibili, pesandoli in base alla loro plausibilità a posteriori. Questo porta alla formula fondamentale:
\[ p(\tilde{y} \mid y) = \int p(\tilde{y} \mid \theta)\, p(\theta \mid y)\, d\theta . \tag{52.1}\]
52.1.4 Interpretazione
La distribuzione predittiva a posteriori \(p(\tilde{y} \mid y)\) rappresenta la miglior stima possibile della probabilità di un dato futuro: tiene conto sia dell’incertezza sui parametri sia della variabilità del fenomeno stesso.
52.2 Caso discreto
Se \(\theta\) può assumere un numero finito di valori, l’integrale si riduce a una somma:
\[ p(\tilde{y} \mid y) = \sum_{\theta} p(\tilde{y} \mid \theta)\, p(\theta \mid y). \tag{52.2}\]
Questo approccio è particolarmente utile nei modelli discreti o quando lavoriamo con approssimazioni basate su campioni finiti di valori di \(\theta\) (ad esempio, i campioni MCMC).
52.3 Il caso Beta–Binomiale
Consideriamo un esperimento binomiale: lanciamo una moneta \(n\) volte e osserviamo il numero di successi \(y\) (ad esempio, il numero di teste). In ottica bayesiana, l’analisi segue tre passaggi fondamentali:
-
Distribuzione a priori Prima di osservare i dati, esprimiamo le nostre conoscenze (o incertezze) sulla probabilità di successo \(p\). Una scelta comune è la distribuzione Beta(\(\alpha, \beta\)), perché è definita sull’intervallo \([0,1]\) e molto flessibile:
- \(\alpha\) si può interpretare come un numero “fittizio” di successi già osservati;
- \(\beta\) come un numero “fittizio” di insuccessi.
In questo modo, la prior sintetizza eventuali conoscenze pregresse sotto forma di “dati immaginari”.
-
Distribuzione a posteriori Dopo aver osservato \(y\) successi su \(n\) prove, aggiorniamo la prior con i dati tramite la regola di Bayes. Poiché la Beta è coniugata alla Binomiale, la distribuzione a posteriori ha ancora forma Beta, con parametri aggiornati:
\[ \alpha_{\text{post}} = \alpha_{\text{prior}} + y, \quad \beta_{\text{post}} = \beta_{\text{prior}} + (n - y). \]
Questa distribuzione descrive ciò che sappiamo su \(p\) dopo aver osservato i dati.
-
Distribuzione predittiva a posteriori Se vogliamo prevedere il numero di successi futuri \(y_{\text{new}}\) in un nuovo esperimento con \(n_{\text{new}}\) prove, dobbiamo combinare:
- l’incertezza residua su \(p\), descritta dalla distribuzione a posteriori;
- la variabilità del processo binomiale per le nuove osservazioni.
In pratica:
- estraiamo \(p \sim \text{Beta}(\alpha_{\text{post}}, \beta_{\text{post}})\);
- generiamo \(y_{\text{new}} \sim \text{Binomiale}(n_{\text{new}}, p)\).
Questo procedimento produce la distribuzione predittiva a posteriori, che integra entrambe le fonti di incertezza.
52.4 Un esempio numerico
52.4.1 Parametri osservati e prior
- Dati: \(y = 70\) successi su \(n = 100\) prove.
- Prior: Beta(2, 2), debolmente informativa, con leggera preferenza per valori di \(p\) vicini a 0.5.
52.4.2 Distribuzione a posteriori
Aggiornando la prior:
\[ \alpha_{\text{post}} = 2 + 70 = 72, \quad \beta_{\text{post}} = 2 + (100 - 70) = 32. \]
La distribuzione a posteriori è quindi \(p \sim \text{Beta}(72, 32)\), centrata attorno a \(p \approx 0.7\).
52.4.3 Simulazione predittiva
Supponiamo di voler prevedere \(y_{\text{new}}\) su \(n_{\text{new}} = 10\) prove:
set.seed(123)
# Dati osservati
y <- 70
n <- 100
# Prior
alpha_prior <- 2
beta_prior <- 2
# Posterior
alpha_post <- alpha_prior + y
beta_post <- beta_prior + (n - y)
# Campioni da p|y ~ Beta(72, 32)
p_samples <- rbeta(1000, alpha_post, beta_post)
# Simulazione di successi futuri
y_preds <- rbinom(1000, size = 10, prob = p_samples)
# Proporzioni di successi
prop_preds <- y_preds / 1052.4.4 Spiegazione del codice
1. Distribuzione a posteriori di \(p\).
alpha_post <- alpha_prior + y
beta_post <- beta_prior + (n - y)
p_samples <- rbeta(1000, alpha_post, beta_post)Qui calcoliamo la distribuzione a posteriori di \(p\): \(p \mid y \sim \text{Beta}(72, 32)\). Con rbeta(1000, 72, 32) estraiamo 1000 campioni da questa distribuzione: ognuno rappresenta un valore plausibile della probabilità di successo \(p\), pesato implicitamente dalla distribuzione a posteriori. In altre parole, stiamo implementando il concetto: non conosciamo il vero \(p\), ma lo trattiamo come una variabile aleatoria distribuita secondo la posterior.
2. Distribuzione predittiva di nuovi dati.
y_preds <- rbinom(1000, size = 10, prob = p_samples)Per ogni valore di \(p\) campionato dalla posterior, simuliamo un nuovo esperimento con 10 prove (rbinom). Questa parte del codice riflette l’integrale teorico della distribuzione predittiva:
\[ p(\tilde{y} \mid y) = \int p(\tilde{y} \mid p)\, p(p \mid y)\, dp . \]
In pratica, invece di calcolare l’integrale, lo approssimiamo con simulazioni:
- per ciascun \(p\) plausibile (estratto dalla posterior),
- generiamo un possibile esito futuro \(\tilde{y}\),
- ripetiamo il processo tante volte.
Così otteniamo un campione dalla distribuzione predittiva a posteriori.
3. Proporzioni di successi.
prop_preds <- y_preds / 10Convertiamo i conteggi di successi in proporzioni: ogni valore rappresenta un possibile esito futuro, considerando sia l’incertezza su \(p\) sia la variabilità intrinseca del processo binomiale.
4. Legame con l’idea teorica.
L’idea era:
“Poiché non conosciamo il vero valore di \(p\), consideriamo tutti i valori possibili, pesandoli in base alla loro plausibilità a posteriori.”
Il codice fa esattamente questo:
- con
rbeta()campioniamo valori plausibili di \(p\) dalla distribuzione a posteriori (il “peso” viene dal fatto che valori più probabili vengono campionati più spesso); - con
rbinom()generiamo i dati futuri \(\tilde{y}\) per ognuno di questi valori.
Il risultato (prop_preds) è un insieme di possibili esiti futuri che incorpora entrambe le fonti di incertezza:
- l’incertezza residua sul parametro \(p\) (posterior),
- la variabilità del processo binomiale (dati futuri).
52.4.5 Visualizzazione
Distribuzione a priori:
curve(dbeta(x, alpha_prior, beta_prior), from = 0, to = 1,
main = "Distribuzione a Priori", col = "blue", lwd = 2, ylab = "Densità")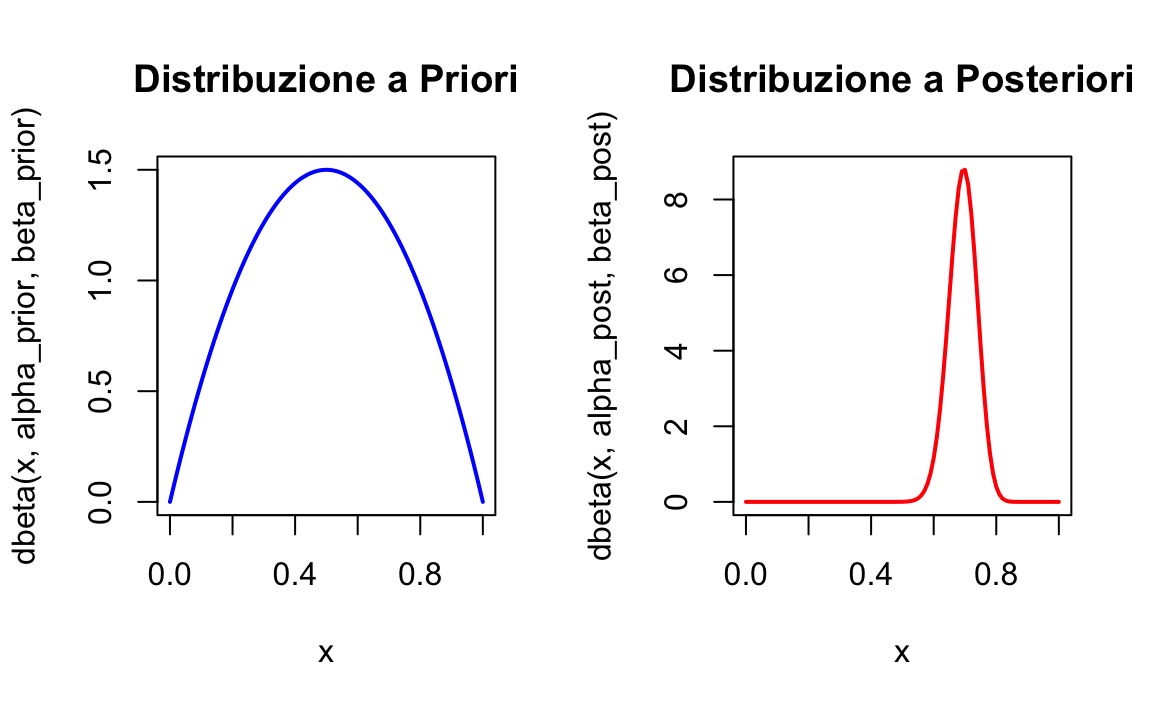
Distribuzione a posteriori:
curve(dbeta(x, alpha_post, beta_post), from = 0, to = 1,
main = "Distribuzione a Posteriori", col = "red", lwd = 2, ylab = "Densità")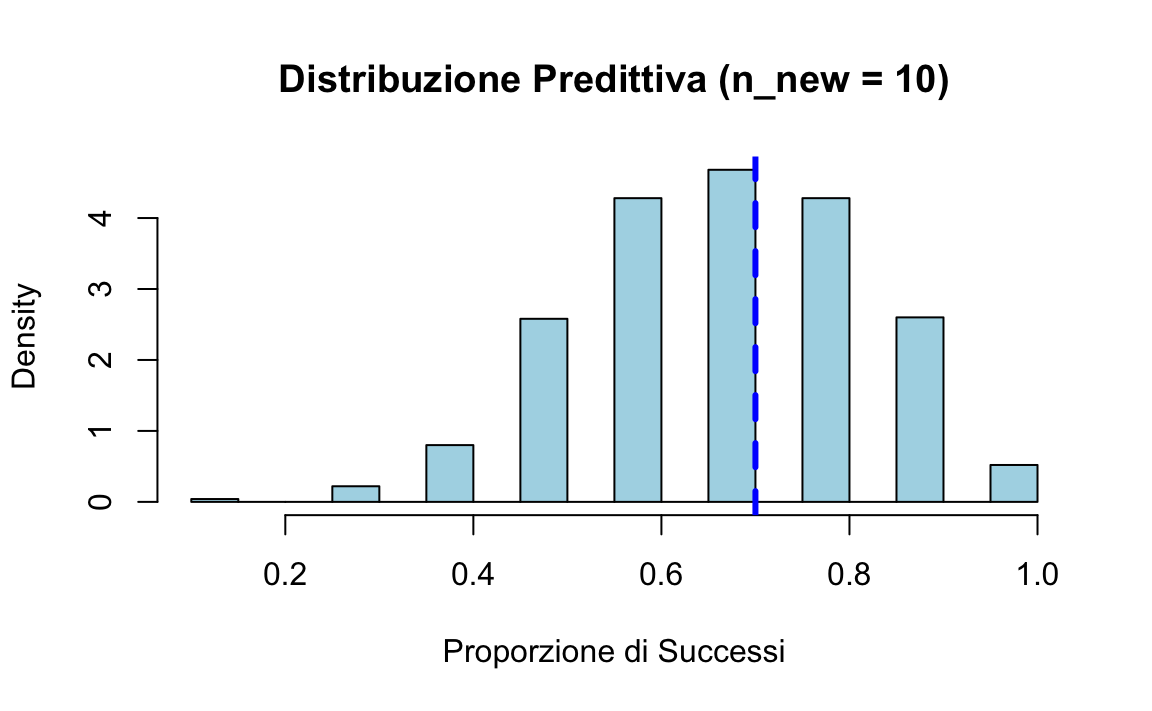
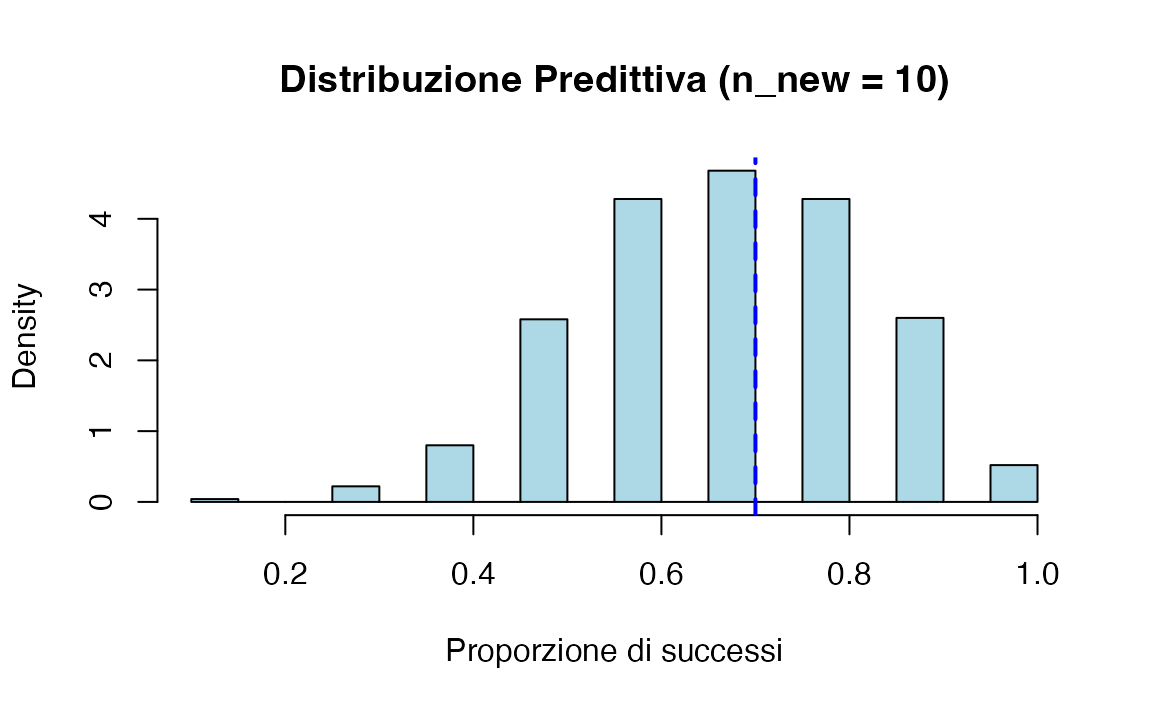
Distribuzione predittiva per \(n_{\text{new}} = 10\):
52.4.6 Interpretazione
- La distribuzione a posteriori \(p \sim \text{Beta}(72, 32)\) è stretta attorno a 0.7, riflettendo l’elevata informazione contenuta nei 100 lanci osservati.
- La distribuzione predittiva per \(n_{\text{new}} = 10\) è invece più ampia: la ridotta numerosità introduce ulteriore variabilità oltre all’incertezza residua su \(p\).
- L’istogramma mostra che i valori più probabili per la proporzione futura oscillano intorno a 0.7, ma con maggiore dispersione.
La distribuzione predittiva a posteriori consente di verificare se il modello è in grado di generare dati simili a quelli osservati.
Nel nostro caso, la proporzione osservata (\(0.7\)) cade vicino al centro della distribuzione predittiva: ciò indica che il modello riproduce bene i dati e può essere utilizzato con fiducia per fare previsioni.
Riflessioni conclusive
La distribuzione predittiva a posteriori è il fulcro dell’inferenza bayesiana, non solo per la sua capacità di generare previsioni robuste sui dati futuri, ma soprattutto perché integra intrinsecamente l’incertezza sui parametri del modello con la variabilità stocastica del processo. Questa sintesi di incertezze offre un quadro probabilistico completo, superando la mera stima puntuale dei parametri e fornendo una base solida per il confronto diretto tra le aspettative del modello e le evidenze empiriche.
Nel flusso di lavoro bayesiano, la distribuzione predittiva a posteriori si rivela indispensabile per la valutazione del modello. Attraverso i controlli predittivi a posteriori, permette di identificare sistematicamente le discrepanze tra i dati osservati e quelli simulati dal modello. Questi controlli non sono semplici verifiche, ma strumenti diagnostici cruciali: rivelano problemi di specificazione del modello, la non adeguatezza delle distribuzioni a priori scelte e orientano attivamente il processo iterativo di revisione e miglioramento del modello.
Il caso beta-binomiale ha illustrato con chiarezza come un’incertezza sui parametri (rappresentata dalla distribuzione beta) si traduca in previsioni probabilistiche per eventi futuri (i successi binomiali). L’esempio ha evidenziato come le previsioni non richiedano assunzioni restrittive o non realistiche, ma emergano direttamente dalla propagazione dell’incertezza. Questo approccio non solo quantifica rigorosamente l’incertezza, ma facilita anche la comunicazione trasparente e l’interpretabilità delle previsioni.
In sintesi, la distribuzione predittiva a posteriori è l’elemento che salda l’inferenza parametrica all’analisi predittiva empirica nella modellazione bayesiana. Essa garantisce che il processo inferenziale sia non solo più affidabile e interpretabile, ma anche intrinsecamente più applicabile a scenari complessi del mondo reale, fornendo un ponte essenziale tra la teoria del modello e la sua utilità pratica.
Esercizi
Informazioni sull’ambiente di sviluppo
sessionInfo()
#> R version 4.5.1 (2025-06-13)
#> Platform: aarch64-apple-darwin20
#> Running under: macOS Sequoia 15.6.1
#>
#> Matrix products: default
#> BLAS: /Library/Frameworks/R.framework/Versions/4.5-arm64/Resources/lib/libRblas.0.dylib
#> LAPACK: /Library/Frameworks/R.framework/Versions/4.5-arm64/Resources/lib/libRlapack.dylib; LAPACK version 3.12.1
#>
#> locale:
#> [1] C/UTF-8/C/C/C/C
#>
#> time zone: Europe/Zagreb
#> tzcode source: internal
#>
#> attached base packages:
#> [1] stats graphics grDevices utils datasets methods base
#>
#> other attached packages:
#> [1] pillar_1.11.0 tinytable_0.11.0 patchwork_1.3.1
#> [4] ggdist_3.3.3 tidybayes_3.0.7 bayesplot_1.13.0
#> [7] ggplot2_3.5.2 reliabilitydiag_0.2.1 priorsense_1.1.0
#> [10] posterior_1.6.1 loo_2.8.0 rstan_2.32.7
#> [13] StanHeaders_2.32.10 brms_2.22.0 Rcpp_1.1.0
#> [16] sessioninfo_1.2.3 conflicted_1.2.0 janitor_2.2.1
#> [19] matrixStats_1.5.0 modelr_0.1.11 tibble_3.3.0
#> [22] dplyr_1.1.4 tidyr_1.3.1 rio_1.2.3
#> [25] here_1.0.1
#>
#> loaded via a namespace (and not attached):
#> [1] svUnit_1.0.6 tidyselect_1.2.1 farver_2.1.2
#> [4] fastmap_1.2.0 TH.data_1.1-3 tensorA_0.36.2.1
#> [7] digest_0.6.37 timechange_0.3.0 estimability_1.5.1
#> [10] lifecycle_1.0.4 survival_3.8-3 magrittr_2.0.3
#> [13] compiler_4.5.1 rlang_1.1.6 tools_4.5.1
#> [16] knitr_1.50 bridgesampling_1.1-2 htmlwidgets_1.6.4
#> [19] curl_6.4.0 pkgbuild_1.4.8 RColorBrewer_1.1-3
#> [22] abind_1.4-8 multcomp_1.4-28 withr_3.0.2
#> [25] purrr_1.1.0 grid_4.5.1 stats4_4.5.1
#> [28] colorspace_2.1-1 xtable_1.8-4 inline_0.3.21
#> [31] emmeans_1.11.2 scales_1.4.0 MASS_7.3-65
#> [34] cli_3.6.5 mvtnorm_1.3-3 rmarkdown_2.29
#> [37] ragg_1.4.0 generics_0.1.4 RcppParallel_5.1.10
#> [40] cachem_1.1.0 stringr_1.5.1 splines_4.5.1
#> [43] parallel_4.5.1 vctrs_0.6.5 V8_6.0.5
#> [46] Matrix_1.7-3 sandwich_3.1-1 jsonlite_2.0.0
#> [49] arrayhelpers_1.1-0 systemfonts_1.2.3 glue_1.8.0
#> [52] codetools_0.2-20 distributional_0.5.0 lubridate_1.9.4
#> [55] stringi_1.8.7 gtable_0.3.6 QuickJSR_1.8.0
#> [58] htmltools_0.5.8.1 Brobdingnag_1.2-9 R6_2.6.1
#> [61] textshaping_1.0.1 rprojroot_2.1.0 evaluate_1.0.4
#> [64] lattice_0.22-7 backports_1.5.0 memoise_2.0.1
#> [67] broom_1.0.9 snakecase_0.11.1 rstantools_2.4.0
#> [70] coda_0.19-4.1 gridExtra_2.3 nlme_3.1-168
#> [73] checkmate_2.3.2 xfun_0.52 zoo_1.8-14
#> [76] pkgconfig_2.0.3