6. ✏️ Esercizi#
source("../_common.R")
6.1. Scaling Likert dei dati del questionario ordinale, creazione di un punteggio totale e scaling normativo#
Il Strengths and Difficulties Questionnaire (SDQ) è un breve questionario di screening comportamentale riguardante bambini e adolescenti di età compresa tra 3 e 16 anni. Esiste in diverse versioni consultabili su http://www.sdqinfo.org/. Dal sito è possibile scaricare il questionario, il metodo di scoring e le norme del test.
La versione autovalutativa (SDQ Pupil) include 25 item che misurano 5 scale (faccette), con 5 item ciascuna:
Sintomi Emotivi somatico preoccupazioni triste attaccamento paura
Problemi di Condotta scatti ubbidisce* litiga mente ruba
Iperattività irrequietezza agitato distratto riflessivo* attento*
Problemi con i Peer solitario amico* popolare* vittima di bullismo vecchio migliore amico
Pro-sociale prendersi cura condivide gentilezza aiuta
Ai partecipanti viene chiesto di valutare ciascuna domanda utilizzando le seguenti opzioni di risposta: 0 = “Non vero” 1 = “Un po’ vero” 2 = “Certamente vero”
NOTA che alcuni item del SDQ sono reverse: item a punteggio invertito – punteggi più alti della scala corrispondono a punteggi inferiori degli item. Ad esempio, l’item “Di solito faccio quello che mi dicono” (variabile ubbidisce) è reverse dei Problemi di Condotta. Ci sono 5 item di questo tipo nel SDQ; sono contrassegnati nella tabella sopra con asterischi (*).
I partecipanti a questo studio sono alunni di seconda media della stessa scuola (N=228). Si tratta di un campione di comunità e non ci aspettiamo che molti bambini abbiano punteggi al di sopra delle soglie cliniche. Il SDQ è stato somministrato due volte, la prima volta quando i bambini hanno appena iniziato la scuola secondaria (erano in anno 7), e un anno dopo (erano in anno 8).
6.2. Emotional Symptoms scale#
Questa scala non contiene item reverse.
Importiamo i dati in R.
load("../data/data_sdq/SDQ.RData")
glimpse(SDQ)
Rows: 228
Columns: 51
$ Gender <dbl> 1, 1, 1, 1, 1, 1, 1, 1, 1, 1, 1, 1, 1, 1, 1, 1, 1, 1, 1, 1, 1…
$ consid <dbl> 1, 2, 2, 2, 0, 2, 2, 2, 2, 2, 2, 2, 2, 2, 2, 2, 1, 2, 2, 2, 2…
$ restles <dbl> 2, 0, 0, 0, 1, 0, 2, 1, 2, 0, 1, 1, 0, 1, 0, 2, 0, 1, 1, 1, 0…
$ somatic <dbl> 2, 2, 0, 0, 2, 1, 0, 0, 1, 0, 0, 2, 0, 0, 1, 2, 1, 1, 1, 1, 1…
$ shares <dbl> 1, 1, 2, 2, 0, 2, 2, 2, 2, 2, 1, 2, 2, 2, 2, 2, 1, 2, 1, 2, 2…
$ tantrum <dbl> 0, 0, 0, 0, 1, 0, 2, 0, 2, 0, 0, 1, 0, 1, 1, 2, 0, 1, 1, 1, 0…
$ loner <dbl> 0, 0, 0, 0, 0, 0, 0, 2, 2, 0, 0, 1, 0, 0, 0, 1, 0, 0, 2, 2, 0…
$ obeys <dbl> 2, 2, 2, 2, 0, 2, 2, 2, 2, 2, 1, 1, 2, 2, 1, 2, 2, 2, 1, 2, 2…
$ worries <dbl> 1, 0, 0, 0, 1, 0, 1, 0, 0, 0, 0, 2, 0, 1, 2, 0, 1, 1, 2, 1, 0…
$ caring <dbl> 2, 2, 2, 1, 2, 2, 2, 2, 2, 2, 1, 2, 2, 2, 2, 2, 1, 2, 2, 1, 2…
$ fidgety <dbl> 0, 0, 0, 0, 0, 0, 2, 0, 0, 0, 1, 1, 0, 0, 0, 1, 0, 0, 0, 1, 0…
$ friend <dbl> 2, 2, 2, 2, 0, 2, 2, 2, 2, 2, 1, 2, 2, 2, 2, 2, 2, 2, 1, 2, 2…
$ fights <dbl> 0, 0, 0, 0, 0, 0, 0, 0, 0, 0, 0, 0, 0, 0, 0, 0, 0, 0, 0, 0, 0…
$ unhappy <dbl> 0, 0, 0, 0, 0, 0, 1, 0, 0, 0, 0, 1, 0, 0, 1, 0, 0, 0, 2, 1, 0…
$ popular <dbl> 2, 2, 2, 1, 1, 2, 2, 2, 2, 2, 2, 2, 1, 1, 1, 2, 1, 2, 1, 1, 2…
$ distrac <dbl> 0, 1, 0, 0, 1, 0, 2, 0, 0, 0, 0, 1, 0, 0, 1, 2, 0, 0, 1, 0, 0…
$ clingy <dbl> 1, 1, 0, 1, 1, 1, 2, 0, 0, 0, 0, 1, 0, 2, 2, 1, 2, 0, 2, 2, 0…
$ kind <dbl> 1, 2, 2, 2, 1, 2, 2, 2, 2, 1, 1, 2, 2, 2, 2, 2, 1, 2, 2, 2, 2…
$ lies <dbl> 0, 0, 0, 0, 2, 0, 1, 0, 2, 0, 0, 1, 0, 0, 1, 0, 0, 0, 0, 0, 0…
$ bullied <dbl> 0, 0, 0, 0, 2, 0, 1, 0, 0, 0, 0, 1, 0, 0, 1, 0, 0, 0, 1, 1, 0…
$ helpout <dbl> 2, 1, 2, 2, 0, 2, 2, 2, 1, 2, 1, 2, 2, 1, 2, 2, 1, 2, 1, 2, 2…
$ reflect <dbl> 1, 1, 2, 2, 0, 2, 2, 2, 1, 1, 1, 1, 1, 1, 1, 2, 2, 2, 1, 1, 2…
$ steals <dbl> 0, 0, 0, 0, 0, 0, 0, 0, 0, 0, 1, 0, 0, 0, 1, 0, 0, 0, 0, 0, 0…
$ oldbest <dbl> 1, 0, 2, 1, 0, 1, 1, 1, 0, 0, 0, 1, 0, 0, 1, 1, 0, 0, 2, 1, 1…
$ afraid <dbl> 0, 0, 1, 1, 0, 0, 0, 0, 0, 1, 0, 2, 2, 0, 1, 1, 1, 0, 1, 1, 0…
$ attends <dbl> 2, 2, 1, 2, 0, 2, 2, 2, 2, 2, 1, 1, 2, 1, 2, 2, 1, 1, 1, 1, 2…
$ consid2 <dbl> 1, 2, 2, 2, NA, 2, 2, 2, 2, 2, NA, 1, NA, 2, 2, NA, 1, 2, 2, …
$ restles2 <dbl> 0, 1, 2, 1, NA, 0, 1, 1, 0, 0, NA, 2, NA, 0, 1, NA, 1, 1, 2, …
$ somatic2 <dbl> 0, 1, 1, 0, NA, 0, 0, 0, 0, 0, NA, 2, NA, 0, 1, NA, 0, 1, 2, …
$ shares2 <dbl> 1, 2, 2, 1, NA, 2, 1, 2, 2, 2, NA, 2, NA, 2, 2, NA, 1, 2, 1, …
$ tantrum2 <dbl> 0, 1, 2, 0, NA, 0, 2, 0, 0, 0, NA, 2, NA, 0, 1, NA, 1, 0, 2, …
$ loner2 <dbl> 0, 0, 1, 0, NA, 0, 0, 0, 0, 0, NA, 1, NA, 1, 0, NA, 0, 0, 1, …
$ obeys2 <dbl> 2, 1, 2, 1, NA, 2, 2, 2, 2, 1, NA, 1, NA, 2, 1, NA, 1, 2, 1, …
$ worries2 <dbl> 0, 0, 1, 0, NA, NA, 1, 0, 0, 0, NA, 1, NA, 1, 2, NA, 0, 0, 2,…
$ caring2 <dbl> 2, 2, 1, 2, NA, 2, 2, 2, 2, 2, NA, 2, NA, 2, 2, NA, 1, 2, 2, …
$ fidgety2 <dbl> 0, 1, 0, 0, NA, 0, 1, 0, 0, 0, NA, 2, NA, 0, 0, NA, 1, 0, 2, …
$ friend2 <dbl> 2, 2, 1, 2, NA, 2, 2, 2, 2, 2, NA, 2, NA, 1, 2, NA, 2, 2, 2, …
$ fights2 <dbl> 0, 0, 0, 0, NA, 0, 0, 0, 0, 0, NA, 2, NA, 0, 0, NA, 0, 0, 0, …
$ unhappy2 <dbl> 0, 0, 1, 0, NA, 0, 0, 0, 0, 0, NA, 1, NA, 0, 0, NA, 0, 0, 1, …
$ popular2 <dbl> 2, 1, 1, 2, NA, 2, 1, 2, 2, 2, NA, 2, NA, 2, 2, NA, 1, 2, 1, …
$ distrac2 <dbl> 0, 0, 0, 2, NA, 0, 2, 1, 0, 0, NA, 1, NA, 0, 1, NA, 1, 0, 2, …
$ clingy2 <dbl> 1, 1, 1, 0, NA, 1, 1, 1, 0, 0, NA, 1, NA, 0, 0, NA, 2, 0, 2, …
$ kind2 <dbl> 2, 2, 2, 2, NA, 2, 2, 2, 2, 2, NA, 2, NA, 2, 2, NA, 1, 2, 2, …
$ lies2 <dbl> 1, 0, 0, 0, NA, 0, 1, 0, 1, 0, NA, 1, NA, 0, 0, NA, 1, 0, 0, …
$ bullied2 <dbl> 0, 0, 0, 0, NA, 0, 2, 0, 0, 0, NA, 0, NA, 0, 0, NA, 0, 0, 0, …
$ helpout2 <dbl> 1, 1, 1, 2, NA, 2, 2, 1, 2, 1, NA, 2, NA, 2, 1, NA, 0, 2, 1, …
$ reflect2 <dbl> 1, 1, 2, 1, NA, 2, 1, 2, 1, 2, NA, 1, NA, 2, 1, NA, 1, 2, 1, …
$ steals2 <dbl> 0, 0, 0, 0, NA, 0, 0, 0, 0, 0, NA, 2, NA, 0, 0, NA, 0, 0, 0, …
$ oldbest2 <dbl> 0, 0, 1, 0, NA, 1, 0, 1, 1, 0, NA, 1, NA, 0, 0, NA, 0, 0, 1, …
$ afraid2 <dbl> 0, 1, 0, 0, NA, 0, 0, 0, 0, 0, NA, 2, NA, 0, 0, NA, 0, 0, 2, …
$ attends2 <dbl> 1, 1, 2, 0, NA, 2, 2, 2, 2, 1, NA, 1, NA, 2, 2, NA, 1, 1, 0, …
Selezioniamo solo gli item della Emotional Symptoms scale.
items_emotion <- c("somatic", "worries", "unhappy", "clingy", "afraid")
sdq_emo <- SDQ[, items_emotion]
sdq_emo |>
head()
| somatic | worries | unhappy | clingy | afraid |
|---|---|---|---|---|
| <dbl> | <dbl> | <dbl> | <dbl> | <dbl> |
| 2 | 1 | 0 | 1 | 0 |
| 2 | 0 | 0 | 1 | 0 |
| 0 | 0 | 0 | 0 | 1 |
| 0 | 0 | 0 | 1 | 1 |
| 2 | 1 | 0 | 1 | 0 |
| 1 | 0 | 0 | 1 | 0 |
Calcoliamo il punteggio della scala.
rowSums(sdq_emo)
- 4
- 3
- 1
- 2
- 4
- 2
- 4
- 0
- 1
- 1
- 0
- 8
- 2
- 3
- 7
- 4
- 5
- 2
- 8
- 6
- 1
- 4
- 9
- 4
- 5
- 9
- 0
- 3
- 3
- 1
- 0
- 2
- 6
- 3
- 9
- 4
- 4
- 0
- 7
- 1
- 3
- 6
- 4
- 5
- 4
- 1
- 4
- 1
- 0
- 5
- 1
- 2
- 2
- 4
- 4
- 4
- 6
- 1
- 8
- 3
- 2
- 2
- 4
- 1
- 1
- 0
- 2
- 2
- 7
- 5
- 0
- <NA>
- <NA>
- 1
- 1
- 7
- 4
- 1
- 8
- 3
- 5
- 0
- 5
- 4
- 0
- 1
- 1
- 5
- 3
- 6
- 1
- 3
- 2
- 6
- 6
- 0
- 2
- 4
- 5
- 3
- 3
- 1
- 1
- 7
- 2
- 3
- 5
- 5
- <NA>
- 0
- 4
- 0
- 4
- 1
- 1
- 1
- 1
- 0
- 2
- 7
- 0
- 3
- 8
- 4
- 6
- <NA>
- 2
- 4
- 7
- 1
- 0
- 0
- 1
- 0
- 4
- 3
- 0
- 10
- 5
- 2
- 1
- 6
- 1
- 2
- 1
- 0
- 1
- <NA>
- 4
- 4
- 2
- 4
- 7
- 5
- 6
- 1
- 0
- 5
- 3
- 1
- 3
- 3
- 6
- 4
- 2
- 3
- 1
- 0
- 3
- 3
- 0
- 3
- 0
- 0
- 0
- 2
- 2
- 2
- 0
- 1
- 5
- 3
- 3
- 1
- 4
- 3
- 1
- 6
- 2
- 4
- 2
- <NA>
- 0
- 2
- 5
- 5
- 0
- 2
- 2
- 3
- 4
- 0
- 2
- 4
- 2
- 2
- 1
- 3
- 2
- 0
- 1
- 0
- 0
- 8
- 1
- 1
- 2
- 1
- 2
- 2
- 4
- 0
- 0
- 1
- 2
- 2
- 1
- 6
Notiamo che ci sono diversi punteggi mancanti, denotati da NA.
Un primo metodo per affrontare i dati mancanti è semplicemente quello di ignorarli:
rowSums(sdq_emo, na.rm = TRUE)
- 4
- 3
- 1
- 2
- 4
- 2
- 4
- 0
- 1
- 1
- 0
- 8
- 2
- 3
- 7
- 4
- 5
- 2
- 8
- 6
- 1
- 4
- 9
- 4
- 5
- 9
- 0
- 3
- 3
- 1
- 0
- 2
- 6
- 3
- 9
- 4
- 4
- 0
- 7
- 1
- 3
- 6
- 4
- 5
- 4
- 1
- 4
- 1
- 0
- 5
- 1
- 2
- 2
- 4
- 4
- 4
- 6
- 1
- 8
- 3
- 2
- 2
- 4
- 1
- 1
- 0
- 2
- 2
- 7
- 5
- 0
- 2
- 7
- 1
- 1
- 7
- 4
- 1
- 8
- 3
- 5
- 0
- 5
- 4
- 0
- 1
- 1
- 5
- 3
- 6
- 1
- 3
- 2
- 6
- 6
- 0
- 2
- 4
- 5
- 3
- 3
- 1
- 1
- 7
- 2
- 3
- 5
- 5
- 4
- 0
- 4
- 0
- 4
- 1
- 1
- 1
- 1
- 0
- 2
- 7
- 0
- 3
- 8
- 4
- 6
- 0
- 2
- 4
- 7
- 1
- 0
- 0
- 1
- 0
- 4
- 3
- 0
- 10
- 5
- 2
- 1
- 6
- 1
- 2
- 1
- 0
- 1
- 4
- 4
- 4
- 2
- 4
- 7
- 5
- 6
- 1
- 0
- 5
- 3
- 1
- 3
- 3
- 6
- 4
- 2
- 3
- 1
- 0
- 3
- 3
- 0
- 3
- 0
- 0
- 0
- 2
- 2
- 2
- 0
- 1
- 5
- 3
- 3
- 1
- 4
- 3
- 1
- 6
- 2
- 4
- 2
- 4
- 0
- 2
- 5
- 5
- 0
- 2
- 2
- 3
- 4
- 0
- 2
- 4
- 2
- 2
- 1
- 3
- 2
- 0
- 1
- 0
- 0
- 8
- 1
- 1
- 2
- 1
- 2
- 2
- 4
- 0
- 0
- 1
- 2
- 2
- 1
- 6
Tuttavia, questa non è una buona idea. Anche per il fatto che, in questo modo non verrà calcolato il punteggio totale di 7 partecipanti. Possiamo identificare le colonne in cui ci sono dei valori mancanti usando summary().
summary(sdq_emo)
somatic worries unhappy clingy
Min. :0.0000 Min. :0.0000 Min. :0.0000 Min. :0.0000
1st Qu.:0.0000 1st Qu.:0.0000 1st Qu.:0.0000 1st Qu.:0.0000
Median :0.0000 Median :0.0000 Median :0.0000 Median :1.0000
Mean :0.6106 Mean :0.6211 Mean :0.3172 Mean :0.8421
3rd Qu.:1.0000 3rd Qu.:1.0000 3rd Qu.:1.0000 3rd Qu.:1.0000
Max. :2.0000 Max. :2.0000 Max. :2.0000 Max. :2.0000
NA's :2 NA's :1 NA's :1
afraid
Min. :0.00
1st Qu.:0.00
Median :0.00
Mean :0.48
3rd Qu.:1.00
Max. :2.00
NA's :3
sdq_emo <- sdq_emo %>%
mutate_at(vars(somatic:afraid), ~ ifelse(is.na(.), mean(., na.rm = TRUE), .))
Questa istruzione utilizza la funzione mutate_at del pacchetto dplyr per applicare una trasformazione a colonne specifiche (da somatic a afraid). All’interno della funzione di trasformazione, essa controlla se ogni valore è mancante (NA). Se lo è, lo sostituisce con la media della colonna usando mean(., na.rm = TRUE), che calcola la media escludendo eventuali valori mancanti.
Possiamo ora calcolare il punteggio della scala per ciascun partecipante.
SDQ$s_emotion <- rowSums(sdq_emo)
SDQ$s_emotion
- 4
- 3
- 1
- 2
- 4
- 2
- 4
- 0
- 1
- 1
- 0
- 8
- 2
- 3
- 7
- 4
- 5
- 2
- 8
- 6
- 1
- 4
- 9
- 4
- 5
- 9
- 0
- 3
- 3
- 1
- 0
- 2
- 6
- 3
- 9
- 4
- 4
- 0
- 7
- 1
- 3
- 6
- 4
- 5
- 4
- 1
- 4
- 1
- 0
- 5
- 1
- 2
- 2
- 4
- 4
- 4
- 6
- 1
- 8
- 3
- 2
- 2
- 4
- 1
- 1
- 0
- 2
- 2
- 7
- 5
- 0
- 2.48
- 7.62114537444934
- 1
- 1
- 7
- 4
- 1
- 8
- 3
- 5
- 0
- 5
- 4
- 0
- 1
- 1
- 5
- 3
- 6
- 1
- 3
- 2
- 6
- 6
- 0
- 2
- 4
- 5
- 3
- 3
- 1
- 1
- 7
- 2
- 3
- 5
- 5
- 5.09061946902655
- 0
- 4
- 0
- 4
- 1
- 1
- 1
- 1
- 0
- 2
- 7
- 0
- 3
- 8
- 4
- 6
- 0.317180616740088
- 2
- 4
- 7
- 1
- 0
- 0
- 1
- 0
- 4
- 3
- 0
- 10
- 5
- 2
- 1
- 6
- 1
- 2
- 1
- 0
- 1
- 4.48
- 4
- 4
- 2
- 4
- 7
- 5
- 6
- 1
- 0
- 5
- 3
- 1
- 3
- 3
- 6
- 4
- 2
- 3
- 1
- 0
- 3
- 3
- 0
- 3
- 0
- 0
- 0
- 2
- 2
- 2
- 0
- 1
- 5
- 3
- 3
- 1
- 4
- 3
- 1
- 6
- 2
- 4
- 2
- 4.61061946902655
- 0
- 2
- 5
- 5
- 0
- 2
- 2
- 3
- 4
- 0
- 2
- 4
- 2
- 2
- 1
- 3
- 2
- 0
- 1
- 0
- 0
- 8
- 1
- 1
- 2
- 1
- 2
- 2
- 4
- 0
- 0
- 1
- 2
- 2
- 1
- 6
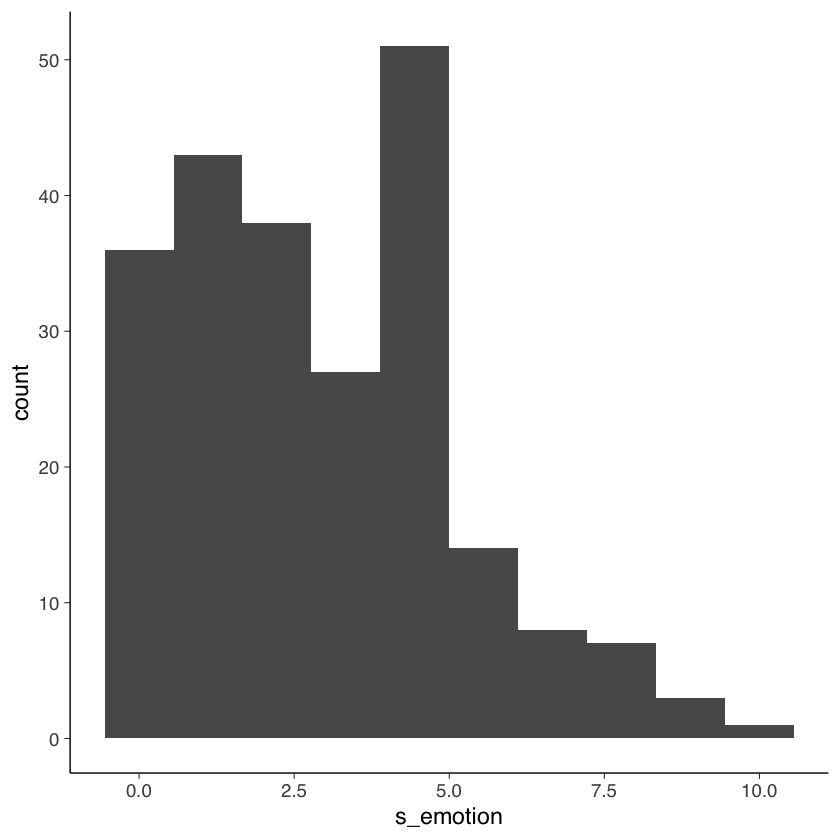
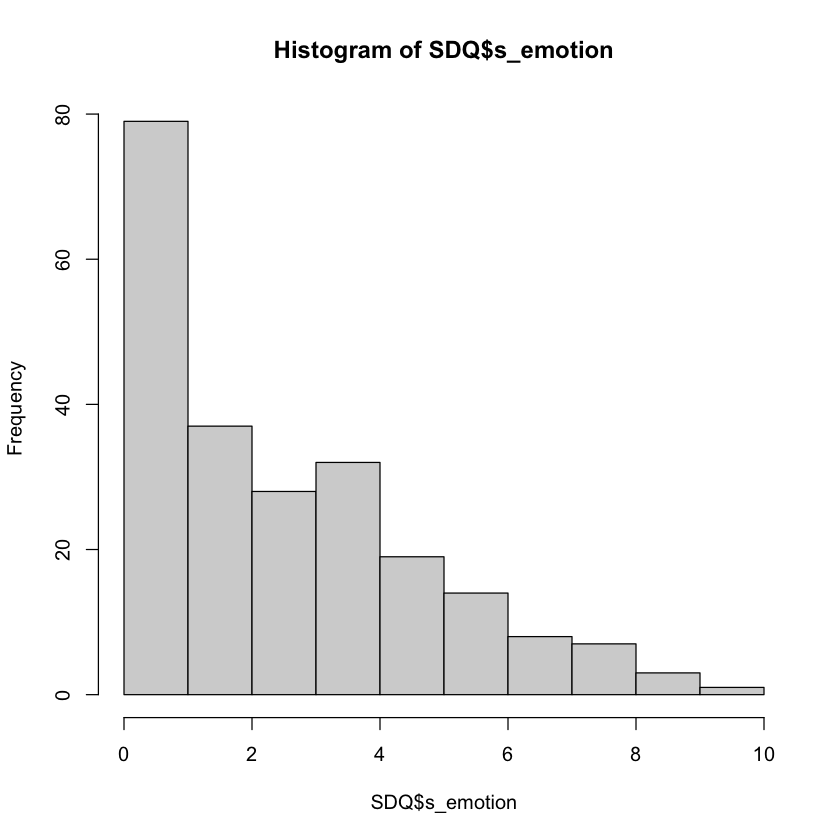
Un istogramma si ottiene nel modo seguente.
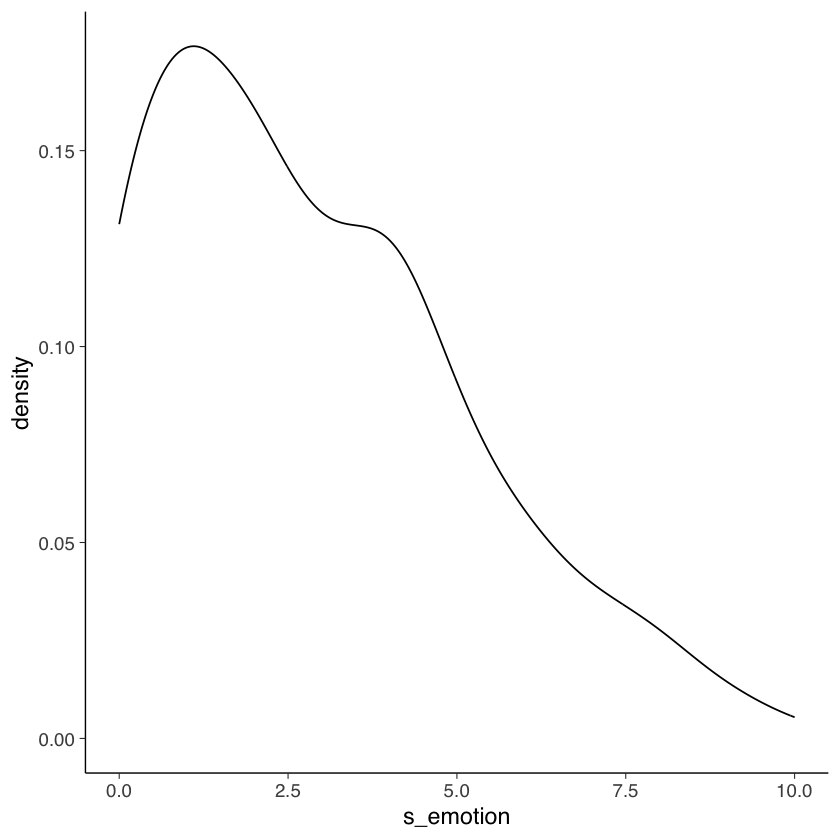
Più utile è un KDE plot.
Possiamo ottenere le statistiche descrittive della scala usando la funzione describe del pacchetto psych.
describe(SDQ$s_emotion)
| vars | n | mean | sd | median | trimmed | mad | min | max | range | skew | kurtosis | se | |
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| <dbl> | <dbl> | <dbl> | <dbl> | <dbl> | <dbl> | <dbl> | <dbl> | <dbl> | <dbl> | <dbl> | <dbl> | <dbl> | |
| X1 | 1 | 228 | 2.871051 | 2.308943 | 2 | 2.652057 | 2.9652 | 0 | 10 | 10 | 0.7163348 | -0.1515175 | 0.1529135 |
Come si può vedere, la mediana (il punteggio al di sotto del quale si trova la metà del campione) di s_emotion è 2, mentre la media è più alta e pari a 2.87. Questo perché la distribuione dei punteggi è asimmetrica positiva; in questo caso, la mediana è più rappresentativa della tendenza centrale. Queste statistiche sono coerenti con la nostra osservazione dell’istogramma, che mostra un forte floor effect.
Di seguito sono riportati i valori di soglia per i casi “Normali”, “Borderline” e “Anormali” per i Sintomi Emotivi forniti dal publisher del test (vedi https://sdqinfo.org/). Questi sono i punteggi che distinguono i casi probabilmente borderline e anormali dai casi “normali”.
Normale: 0-5 Borderline: 6 Anormale: 7-10
table(SDQ$s_emotion <= 5)
FALSE TRUE
33 195
In questo campione, dunque, l’85% dei partecipanti è classificato nell’intervallo Normale.
table(SDQ$s_emotion <= 5)[2] / length(SDQ$s_emotion)
In maniera equivalente otteniamo
table(SDQ$s_emotion == 6)[2] / length(SDQ$s_emotion)
table(SDQ$s_emotion >= 7)[2] / length(SDQ$s_emotion)
6.3. Item reverse#
La scala Conduct Problems contiene item reverse. Esaminiamo lo scoring di questo tipo di item.
items_conduct <- c("tantrum", "obeys", "fights", "lies", "steals")
Per i Problemi di Condotta, abbiamo solo un item reverse, obeys.
tantrum obeys* fights lies steals
Per invertire il codice di questo item, useremo una funzione dedicata del pacchetto psych, reverse.code(). Questa funzione ha la forma generale reverse.code(keys, items,…). L’argomento keys è un vettore di valori 1 o -1, dove -1 implica l’inversione dell’item. L’argomento items sono i nomi delle variabili che vogliamo valutare.
R_conduct <- reverse.code(keys = c(1, -1, 1, 1, 1), SDQ[, items_conduct]) |> as.data.frame()
R_conduct |> head()
| tantrum | obeys- | fights | lies | steals | |
|---|---|---|---|---|---|
| <dbl> | <dbl> | <dbl> | <dbl> | <dbl> | |
| 1 | 0 | 0 | 0 | 0 | 0 |
| 2 | 0 | 0 | 0 | 0 | 0 |
| 3 | 0 | 0 | 0 | 0 | 0 |
| 4 | 0 | 0 | 0 | 0 | 0 |
| 5 | 1 | 2 | 0 | 2 | 0 |
| 6 | 0 | 0 | 0 | 0 | 0 |
SDQ[, items_conduct] |> head()
| tantrum | obeys | fights | lies | steals |
|---|---|---|---|---|
| <dbl> | <dbl> | <dbl> | <dbl> | <dbl> |
| 0 | 2 | 0 | 0 | 0 |
| 0 | 2 | 0 | 0 | 0 |
| 0 | 2 | 0 | 0 | 0 |
| 0 | 2 | 0 | 0 | 0 |
| 1 | 0 | 0 | 2 | 0 |
| 0 | 2 | 0 | 0 | 0 |
Anche in questo caso ci sono dei dati mancanti.
summary(R_conduct)
tantrum obeys- fights lies
Min. :0.0000 Min. :0.0000 Min. :0.000 Min. :0.0000
1st Qu.:0.0000 1st Qu.:0.0000 1st Qu.:0.000 1st Qu.:0.0000
Median :0.0000 Median :1.0000 Median :0.000 Median :0.0000
Mean :0.5708 Mean :0.5789 Mean :0.193 Mean :0.5442
3rd Qu.:1.0000 3rd Qu.:1.0000 3rd Qu.:0.000 3rd Qu.:1.0000
Max. :2.0000 Max. :2.0000 Max. :2.000 Max. :2.0000
NA's :2 NA's :2
steals
Min. :0.000
1st Qu.:0.000
Median :0.000
Mean :0.185
3rd Qu.:0.000
Max. :2.000
NA's :1
R_conduct <- R_conduct %>%
mutate_at(vars(tantrum:steals), ~ ifelse(is.na(.), mean(., na.rm = TRUE), .))
Calcoliamo ora il punteggio totale.
SDQ$s_conduct <- rowMeans(R_conduct)
6.4. Session Info#
sessionInfo()
R version 4.3.3 (2024-02-29)
Platform: x86_64-apple-darwin20 (64-bit)
Running under: macOS Sonoma 14.3.1
Matrix products: default
BLAS: /Library/Frameworks/R.framework/Versions/4.3-x86_64/Resources/lib/libRblas.0.dylib
LAPACK: /Library/Frameworks/R.framework/Versions/4.3-x86_64/Resources/lib/libRlapack.dylib; LAPACK version 3.11.0
locale:
[1] en_US.UTF-8/UTF-8/en_US.UTF-8/C/en_US.UTF-8/en_US.UTF-8
time zone: Europe/Rome
tzcode source: internal
attached base packages:
[1] stats graphics grDevices utils datasets methods base
other attached packages:
[1] ggokabeito_0.1.0 viridis_0.6.5 viridisLite_0.4.2 ggpubr_0.6.0
[5] ggExtra_0.10.1 bayesplot_1.11.1 gridExtra_2.3 patchwork_1.2.0
[9] semTools_0.5-6.920 semPlot_1.1.6 lavaan_0.6-17 psych_2.4.1
[13] scales_1.3.0 markdown_1.12 knitr_1.45 lubridate_1.9.3
[17] forcats_1.0.0 stringr_1.5.1 dplyr_1.1.4 purrr_1.0.2
[21] readr_2.1.5 tidyr_1.3.1 tibble_3.2.1 ggplot2_3.5.0
[25] tidyverse_2.0.0 here_1.0.1
loaded via a namespace (and not attached):
[1] rstudioapi_0.15.0 jsonlite_1.8.8 magrittr_2.0.3
[4] TH.data_1.1-2 estimability_1.5 farver_2.1.1
[7] nloptr_2.0.3 rmarkdown_2.26 vctrs_0.6.5
[10] minqa_1.2.6 base64enc_0.1-3 rstatix_0.7.2
[13] htmltools_0.5.7 broom_1.0.5 Formula_1.2-5
[16] htmlwidgets_1.6.4 plyr_1.8.9 sandwich_3.1-0
[19] emmeans_1.10.0 zoo_1.8-12 uuid_1.2-0
[22] igraph_2.0.2 mime_0.12 lifecycle_1.0.4
[25] pkgconfig_2.0.3 Matrix_1.6-5 R6_2.5.1
[28] fastmap_1.1.1 shiny_1.8.0 digest_0.6.34
[31] OpenMx_2.21.11 fdrtool_1.2.17 colorspace_2.1-0
[34] rprojroot_2.0.4 Hmisc_5.1-1 labeling_0.4.3
[37] fansi_1.0.6 timechange_0.3.0 abind_1.4-5
[40] compiler_4.3.3 withr_3.0.0 glasso_1.11
[43] htmlTable_2.4.2 backports_1.4.1 carData_3.0-5
[46] ggsignif_0.6.4 MASS_7.3-60.0.1 corpcor_1.6.10
[49] gtools_3.9.5 tools_4.3.3 pbivnorm_0.6.0
[52] foreign_0.8-86 zip_2.3.1 httpuv_1.6.14
[55] nnet_7.3-19 glue_1.7.0 quadprog_1.5-8
[58] nlme_3.1-164 promises_1.2.1 lisrelToR_0.3
[61] grid_4.3.3 pbdZMQ_0.3-11 checkmate_2.3.1
[64] cluster_2.1.6 reshape2_1.4.4 generics_0.1.3
[67] gtable_0.3.4 tzdb_0.4.0 data.table_1.15.2
[70] hms_1.1.3 car_3.1-2 utf8_1.2.4
[73] sem_3.1-15 pillar_1.9.0 IRdisplay_1.1
[76] rockchalk_1.8.157 later_1.3.2 splines_4.3.3
[79] lattice_0.22-5 survival_3.5-8 kutils_1.73
[82] tidyselect_1.2.0 miniUI_0.1.1.1 pbapply_1.7-2
[85] stats4_4.3.3 xfun_0.42 qgraph_1.9.8
[88] arm_1.13-1 stringi_1.8.3 boot_1.3-29
[91] evaluate_0.23 codetools_0.2-19 mi_1.1
[94] cli_3.6.2 RcppParallel_5.1.7 IRkernel_1.3.2
[97] rpart_4.1.23 xtable_1.8-4 repr_1.1.6
[100] munsell_0.5.0 Rcpp_1.0.12 coda_0.19-4.1
[103] png_0.1-8 XML_3.99-0.16.1 parallel_4.3.3
[106] ellipsis_0.3.2 jpeg_0.1-10 lme4_1.1-35.1
[109] mvtnorm_1.2-4 openxlsx_4.2.5.2 crayon_1.5.2
[112] rlang_1.1.3 multcomp_1.4-25 mnormt_2.1.1