73. Dati longitudinali#
L’obiettivo di questo capitolo è esaminare come è possibile estendere i modelli SEM per adattarli alle particolarità dei dati longitudinali. Per semplificare, cominciamo concentrandoci su due misurazioni temporali consecutive.
73.1. Misurare il cambiamento#
Il modo più semplice per valutare il cambiamento individuale tra due momenti temporali è calcolare la differenza tra i punteggi ottenuti nelle due occasioni. Tuttavia, questa strategia presenta un problema: non conosciamo il vero punteggio dell’individuo nei due momenti temporali, ma solo un punteggio influenzato dall’errore di misurazione. L’errore di misura può ridurre drasticamente la precisione delle valutazioni sulle differenze individuali nel cambiamento.
Per superare il problema dell’errore di misurazione in analisi longitudinali, vengono utilizzati i modelli Latent Growth Models (LGM) nell’ambito dei modelli a equazioni strutturali (SEM).
Questi modelli presuppongono che ciascun individuo segua una traiettoria di cambiamento unica nel tempo. I dati raccolti sono interpretati come la somma di tre componenti:
(a) Punteggi latenti: Rappresentano il livello individuale in un dato momento.
(b) Punteggi di cambiamento latenti: Indicano il cambiamento individuale nel tempo.
(c) Caratteristiche uniche non osservate: Elementi indipendenti delle misurazioni.
Nei modelli SEM, l’equazione fondamentale è espressa come:
dove:
\( \Sigma \) rappresenta la matrice delle varianze e covarianze dedotte dal modello.
\( \Lambda \) indica la matrice dei carichi fattoriali, che descrive le relazioni tra gli indicatori e i costrutti.
\( \Psi \) è la matrice che esprime le varianze e covarianze intercorrenti tra i costrutti.
\( \Theta \) si riferisce alla matrice delle varianze residue, ovvero quei fattori unici, e alle covarianze residue tra gli indicatori.
In un contesto longitudinale, il modello include tre fattori latenti:
un fattore che rappresenta il livello latente in un momento specifico;
un fattore che indica il cambiamento latente tra due momenti;
un fattore per l’errore di misurazione in ciascun momento.
Per esplorare le peculiarità di un modello di misurazione longitudinale, consideriamo il caso dello stesso costrutto misurato in due distinte occasioni temporali. Il punteggio osservato di un individuo in un tempo specifico è dato da:
dove \(\tau_i\) rappresenta il livello latente dell’individuo \(i\) al tempo iniziale, \(\xi_1\) rappresenta il carico del fattore comune per il livello latente al tempo \(t_1\), \(\xi_2\) rappresenta il carico del fattore comune che rappresenta il cambiamento latente tra i due momenti, e \(\delta_{it}\) rappresenta l’errore di misura specifico del momento \(t\) per l’individuo \(i\).
In questo modello, le intercette osservate sono vincolate a 0, semplificando l’interpretazione e attribuendo la variazione nella variabile dipendente esclusivamente ai fattori latenti di cambiamento.
Se, per esempio, vengono utilizzati 5 indicatori in ciascun momento di misurazione, il modello si articola come segue:
Inoltre, il modello ipotizza che \(\xi_1\) e \(\xi_e\) siano correlati, come indicato nella matrice di inter-correlazione fattoriale
dove \(\phi_{11}\) è la varianza dell’intercetta latente, \(\phi_{22}\) è la varianza della pendenza latente e \(\phi_{21}\) è la covarianza dell’intercetta e della pendenza.
Un elemento distintivo dei modelli longitudinali è la possibilità di correlare le varianze residue degli stessi indicatori misurati in momenti differenti (per esempio, la correlazione tra X1 al Tempo 1 e X1 al Tempo 2). Tale approccio consente di identificare non solo le informazioni condivise dal costrutto attraverso il tempo, ma anche quelle peculiari e specifiche di ogni singolo indicatore in ciascun momento osservato.
Questo approccio permette di esaminare lo sviluppo o il cambiamento di un costrutto latente e dei suoi indicatori nel tempo, offrendo un quadro più accurato e approfondito delle dinamiche di cambiamento.
Il modello di crescita latente definito dalle equazioni precedenti porta a una serie di previsioni sulla struttura delle medie e delle covarianze dei dati osservati. Queste previsioni del modello vengono utilizzate nel contesto della modellizzazione delle equazioni strutturali per calcolare le stime dei parametri e gli indici di adattamento del modello. La struttura delle covarianze (\(\boldsymbol{\Sigma}\)) prevista dal modello di crescita latente è
La Fig. 73.1 mostra il diagramma di percorso del modello LGM che stiamo discutendo.
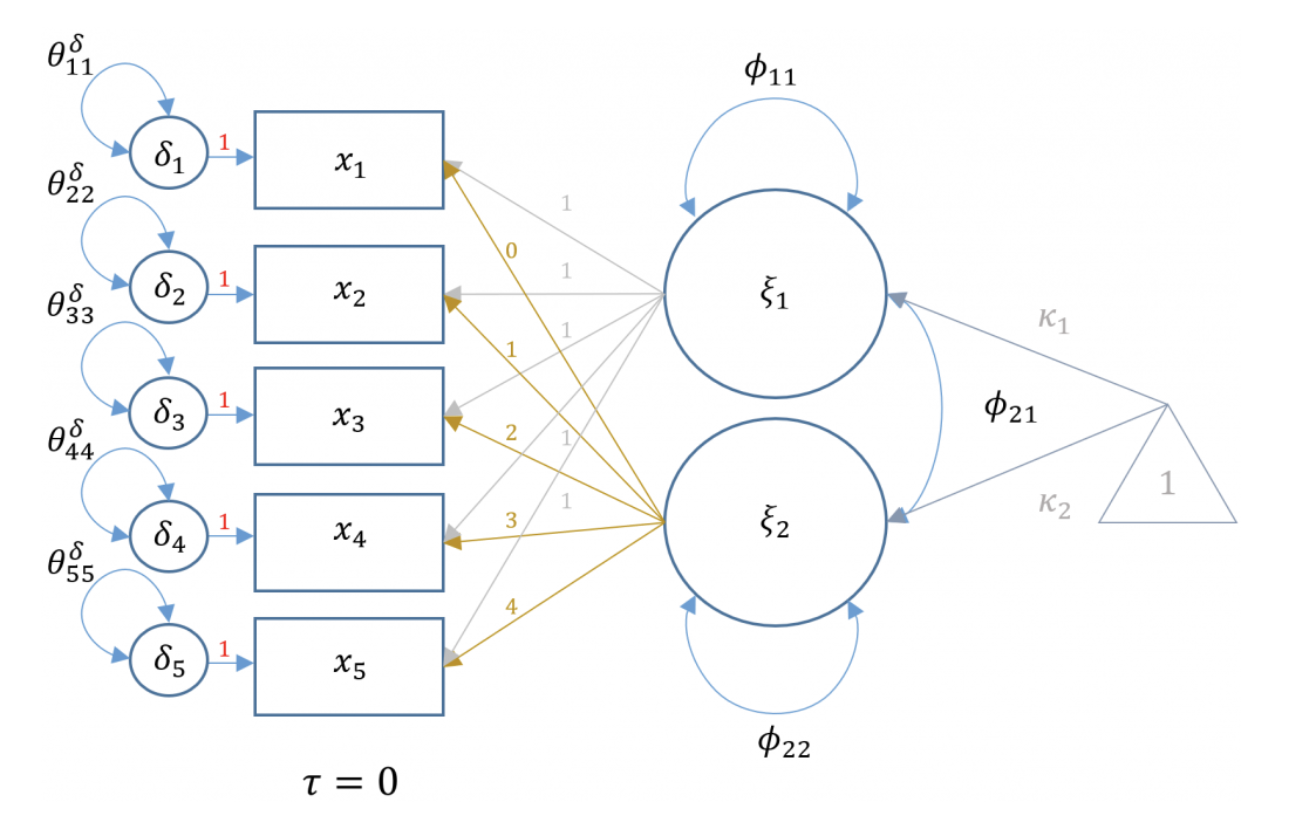
Fig. 73.1 Modello di crescita latente.#
73.2. La Variazione Temporale di Positive Affect#
Applichiamo questo modello al caso in cui tre indicatori di Positive Affect (Glad, Cheerful, Happy) vengono misurati in due momenti del tempo (si veda Little [Lit23]).
Importiamo i dati.
dat <- read.table(
file = "../data/grade7and8.long.823.dat",
col.names = c(
"PAT1P1", "PAT1P2", "PAT1P3", "NAT1P1", "NAT1P2", "NAT1P3",
"PAT2P1", "PAT2P2", "PAT2P3", "NAT2P1", "NAT2P2", "NAT2P3",
"PAT3P1", "PAT3P2", "PAT3P3", "NAT3P1", "NAT3P2", "NAT3P3",
"grade", "female", "black", "hispanic", "other"
)
)
glimpse(dat)
Rows: 823
Columns: 23
$ PAT1P1 <dbl> 1.50000, 2.98116, 3.50000, 3.00000, 3.00000, 3.00000, 3.00000…
$ PAT1P2 <dbl> 1.50000, 2.98284, 4.00000, 3.50000, 2.50000, 2.50000, 2.50000…
$ PAT1P3 <dbl> 2.00000, 2.98883, 4.00000, 2.50000, 3.00000, 3.00000, 4.00000…
$ NAT1P1 <dbl> 2.50000, 1.56218, 1.50000, 1.50000, 1.00000, 1.50000, 1.00000…
$ NAT1P2 <dbl> 3.50000, 1.45688, 1.00000, 2.00000, 1.00000, 2.50000, 1.00000…
$ NAT1P3 <dbl> 3.00000, 1.65477, 1.00000, 1.50000, 1.00000, 2.50000, 1.00000…
$ PAT2P1 <dbl> 4.00000, 4.00000, 4.00000, 2.95942, 3.17170, 2.00000, 3.00000…
$ PAT2P2 <dbl> 4.00000, 4.00000, 2.50000, 2.99083, 2.87806, 2.00000, 3.00000…
$ PAT2P3 <dbl> 4.00000, 4.00000, 4.00000, 3.06670, 3.11031, 3.00000, 4.00000…
$ NAT2P1 <dbl> 2.00000, 1.00000, 1.00000, 1.65159, 1.65777, 2.00000, 1.00000…
$ NAT2P2 <dbl> 1.00000, 1.00000, 1.00000, 1.42599, 1.44804, 2.00000, 1.00000…
$ NAT2P3 <dbl> 2.00000, 1.00000, 1.00000, 1.67184, 1.56296, 2.00000, 1.00000…
$ PAT3P1 <dbl> 4.00000, 4.00000, 4.00000, 4.00000, 2.67109, 3.00000, 2.50000…
$ PAT3P2 <dbl> 4.00000, 4.00000, 4.00000, 3.50000, 2.85851, 2.00000, 2.00000…
$ PAT3P3 <dbl> 4.00000, 4.00000, 3.48114, 3.50000, 3.28099, 2.50000, 3.50000…
$ NAT3P1 <dbl> 1.00000, 1.00000, 1.18056, 1.00000, 1.19869, 2.00000, 1.00000…
$ NAT3P2 <dbl> 1.00000, 1.00000, 1.00000, 1.50000, 1.00000, 2.00000, 1.00000…
$ NAT3P3 <dbl> 2.50000, 1.00000, 1.62051, 1.00000, 1.00000, 3.00000, 1.00000…
$ grade <int> 7, 7, 7, 7, 7, 7, 7, 7, 7, 7, 7, 7, 7, 7, 7, 7, 7, 7, 7, 7, 7…
$ female <int> 2, 1, 2, 1, 1, 1, 2, 1, 1, 1, 2, 1, 1, 1, 2, 1, 2, 2, 2, 1, 1…
$ black <int> 0, 0, 0, 0, 0, 0, 0, 0, 0, 0, 0, 0, 0, 0, 1, 0, 0, 0, 0, 0, 0…
$ hispanic <int> 0, 0, 1, 0, 0, 0, 0, 0, 0, 0, 0, 0, 0, 0, 0, 0, 1, 0, 0, 0, 0…
$ other <int> 0, 1, 0, 0, 0, 0, 0, 0, 0, 0, 0, 0, 0, 0, 0, 0, 0, 0, 1, 0, 0…
La specificazione del modello SEM longitudinale per questi dati in lavaan può essere formulata in modo simile a un modello CFA per un singolo momento del tempo. In questo caso, ci sono due fattori comuni, che chiameremo Fattore_T1 e Fattore_T2, che vengono identificati dagli indicatori misurati nei due momenti del tempo. Questi due fattori comuni sono correlati tra loro.
Tuttavia, la differenza chiave rispetto ai casi precedenti è che anche i fattori specifici di ciascun indicatore nei due momenti del tempo sono correlati tra loro. Questo significa che, oltre alla correlazione tra i fattori comuni Fattore_T1 e Fattore_T2, dobbiamo anche specificare la correlazione tra i fattori specifici dei singoli indicatori nei due momenti del tempo.
mod_1 <- "
# Definizione dei fattori latenti al tempo T1
Fattore_T1 =~ NA*PAT1P1 + PAT1P2 + PAT1P3
# Definizione dei fattori latenti al tempo T2
Fattore_T2 =~ NA*PAT2P1 + PAT2P2 + PAT2P3
# Varianza dei fattori latenti
Fattore_T1 ~~ 1*Fattore_T1
Fattore_T2 ~~ 1*Fattore_T2
# Covarianza tra i fattori latenti
Fattore_T1 ~~ Fattore_T2
# Definizione degli errori di misurazione per gli indicatori al tempo T1
PAT1P1 ~~ PAT1P1
PAT1P2 ~~ PAT1P2
PAT1P3 ~~ PAT1P3
# Definizione degli errori di misurazione per gli indicatori al tempo T2
PAT2P1 ~~ PAT2P1
PAT2P2 ~~ PAT2P2
PAT2P3 ~~ PAT2P3
# Covarianze tra i residui degli item tra T1 e T2
PAT1P1 ~~ PAT2P1
PAT1P2 ~~ PAT2P2
PAT1P3 ~~ PAT2P3
# Opzionale: Specifica delle medie degli indicatori (intercette)
PAT1P1 ~ 1
PAT1P2 ~ 1
PAT1P3 ~ 1
PAT2P1 ~ 1
PAT2P2 ~ 1
PAT2P3 ~ 1
"
Le covarianze tra gli errori degli indicatori corrispondenti tra T1 e T2 vengono stimate, indicando potenziali correlazioni tra gli errori degli stessi indicatori nei due momenti temporali.
In questo modello, i carichi fattoriali e le intercettazioni non sono ancora eguagliati nel tempo, il che significa che ogni set di indicatori è libero di avere relazioni uniche con il proprio fattore latente in ciascun momento temporale.
Questo modello è definito “configural-invariant” perché mantiene la stessa struttura fattoriale (o configurazione) nel tempo, ma non impone ancora l’equivalenza dei parametri tra i due momenti temporali.
Il modello configural-invariant è spesso il punto di partenza per testare l’invarianza longitudinale nei SEM, poiché stabilisce una base di confronto prima di imporre vincoli più stringenti come l’invarianza dei carichi fattoriali o delle intercette nei modelli successivi.
Adattiamo il modello ai dati.
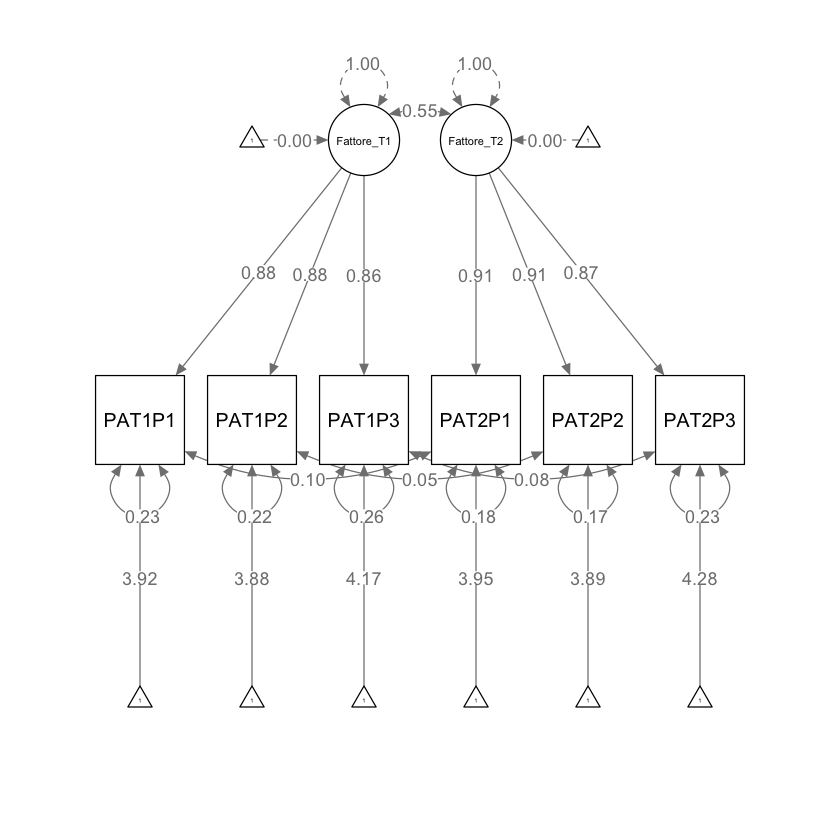
fit_1 <- lavaan::sem(mod_1, data = dat, meanstructure = TRUE)
parameterEstimates(fit_1) |> print()
lhs op rhs est se z pvalue ci.lower ci.upper
1 Fattore_T1 =~ PAT1P1 0.670 0.022 30.862 0.000 0.628 0.713
2 Fattore_T1 =~ PAT1P2 0.661 0.021 31.241 0.000 0.619 0.702
3 Fattore_T1 =~ PAT1P3 0.643 0.021 29.979 0.000 0.601 0.685
4 Fattore_T2 =~ PAT2P1 0.689 0.021 32.994 0.000 0.648 0.730
5 Fattore_T2 =~ PAT2P2 0.680 0.021 33.049 0.000 0.639 0.720
6 Fattore_T2 =~ PAT2P3 0.639 0.021 31.155 0.000 0.598 0.679
7 Fattore_T1 ~~ Fattore_T1 1.000 0.000 NA NA 1.000 1.000
8 Fattore_T2 ~~ Fattore_T2 1.000 0.000 NA NA 1.000 1.000
9 Fattore_T1 ~~ Fattore_T2 0.552 0.027 20.141 0.000 0.498 0.606
10 PAT1P1 ~~ PAT1P1 0.135 0.010 12.919 0.000 0.114 0.155
11 PAT1P2 ~~ PAT1P2 0.121 0.010 12.308 0.000 0.102 0.141
12 PAT1P3 ~~ PAT1P3 0.145 0.010 14.046 0.000 0.125 0.165
13 PAT2P1 ~~ PAT2P1 0.102 0.008 12.160 0.000 0.086 0.119
14 PAT2P2 ~~ PAT2P2 0.098 0.008 11.997 0.000 0.082 0.114
15 PAT2P3 ~~ PAT2P3 0.125 0.009 14.711 0.000 0.108 0.142
16 PAT1P1 ~~ PAT2P1 0.012 0.006 1.946 0.052 0.000 0.025
17 PAT1P2 ~~ PAT2P2 0.005 0.006 0.884 0.377 -0.006 0.017
18 PAT1P3 ~~ PAT2P3 0.011 0.006 1.781 0.075 -0.001 0.024
19 PAT1P1 ~1 2.992 0.027 112.316 0.000 2.940 3.044
20 PAT1P2 ~1 2.896 0.026 111.210 0.000 2.845 2.947
21 PAT1P3 ~1 3.112 0.026 119.527 0.000 3.061 3.163
22 PAT2P1 ~1 3.002 0.026 113.400 0.000 2.950 3.054
23 PAT2P2 ~1 2.909 0.026 111.532 0.000 2.858 2.960
24 PAT2P3 ~1 3.127 0.025 122.862 0.000 3.077 3.177
25 Fattore_T1 ~1 0.000 0.000 NA NA 0.000 0.000
26 Fattore_T2 ~1 0.000 0.000 NA NA 0.000 0.000
semPaths(fit_1,
whatLabels = "std",
sizeMan = 10,
edge.label.cex = 0.9,
style = "mx",
nCharNodes = 0, nCharEdges = 0
)
fitMeasures(fit_1, c("cfi", "tli", "rmsea", "srmr")) |> print()
cfi tli rmsea srmr
1.000 0.999 0.016 0.010
Potremmo pensare che modello di baseline (con cui possono essere confrontati i modelli che descrivono il cambiamento temporale) sia semplicemente il modello in cui non sono permesse covarianze tra i due fattori comuni latenti nei due momenti del tempo.
mod_2 <- "
# Definizione dei fattori latenti al tempo T1
Fattore_T1 =~ NA*PAT1P1 + PAT1P2 + PAT1P3
# Definizione dei fattori latenti al tempo T2
Fattore_T2 =~ NA*PAT2P1 + PAT2P2 + PAT2P3
# Varianza dei fattori latenti
Fattore_T1 ~~ 1*Fattore_T1
Fattore_T2 ~~ 1*Fattore_T2
# Covarianza tra i fattori latenti
Fattore_T1 ~~ 0*Fattore_T2
# Definizione degli errori di misurazione per gli indicatori al tempo T1
PAT1P1 ~~ PAT1P1
PAT1P2 ~~ PAT1P2
PAT1P3 ~~ PAT1P3
# Definizione degli errori di misurazione per gli indicatori al tempo T2
PAT2P1 ~~ PAT2P1
PAT2P2 ~~ PAT2P2
PAT2P3 ~~ PAT2P3
# Covarianze tra i residui degli item tra T1 e T2
# PAT1P1 ~~ PAT2P1
# PAT1P2 ~~ PAT2P2
# PAT1P3 ~~ PAT2P3
# Opzionale: Specifica delle medie degli indicatori (intercette)
PAT1P1 ~ 1
PAT1P2 ~ 1
PAT1P3 ~ 1
PAT2P1 ~ 1
PAT2P2 ~ 1
PAT2P3 ~ 1
"
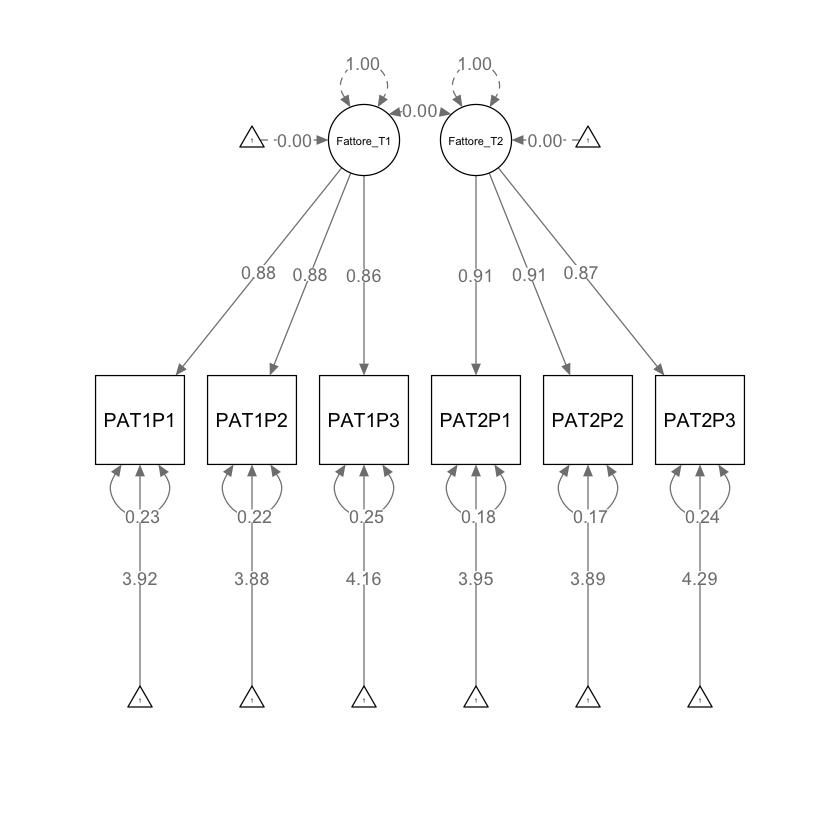
fit_2 <- lavaan::sem(mod_2, data = dat, meanstructure = TRUE)
semPaths(fit_2,
whatLabels = "std",
sizeMan = 10,
edge.label.cex = 0.9,
style = "mx",
nCharNodes = 0, nCharEdges = 0
)
parameterEstimates(fit_2) |> print()
lhs op rhs est se z pvalue ci.lower ci.upper
1 Fattore_T1 =~ PAT1P1 0.670 0.022 30.720 0 0.627 0.713
2 Fattore_T1 =~ PAT1P2 0.658 0.021 30.943 0 0.616 0.700
3 Fattore_T1 =~ PAT1P3 0.647 0.021 30.105 0 0.605 0.689
4 Fattore_T2 =~ PAT2P1 0.689 0.021 32.917 0 0.648 0.730
5 Fattore_T2 =~ PAT2P2 0.681 0.021 33.073 0 0.641 0.722
6 Fattore_T2 =~ PAT2P3 0.636 0.021 30.961 0 0.596 0.676
7 Fattore_T1 ~~ Fattore_T1 1.000 0.000 NA NA 1.000 1.000
8 Fattore_T2 ~~ Fattore_T2 1.000 0.000 NA NA 1.000 1.000
9 Fattore_T1 ~~ Fattore_T2 0.000 0.000 NA NA 0.000 0.000
10 PAT1P1 ~~ PAT1P1 0.135 0.011 12.641 0 0.114 0.156
11 PAT1P2 ~~ PAT1P2 0.125 0.010 12.310 0 0.105 0.145
12 PAT1P3 ~~ PAT1P3 0.141 0.010 13.503 0 0.120 0.161
13 PAT2P1 ~~ PAT2P1 0.102 0.009 11.872 0 0.085 0.119
14 PAT2P2 ~~ PAT2P2 0.097 0.008 11.609 0 0.080 0.113
15 PAT2P3 ~~ PAT2P3 0.127 0.009 14.716 0 0.110 0.144
16 PAT1P1 ~1 2.992 0.027 112.344 0 2.940 3.044
17 PAT1P2 ~1 2.896 0.026 111.246 0 2.845 2.947
18 PAT1P3 ~1 3.112 0.026 119.412 0 3.061 3.163
19 PAT2P1 ~1 3.002 0.026 113.387 0 2.950 3.054
20 PAT2P2 ~1 2.909 0.026 111.468 0 2.858 2.960
21 PAT2P3 ~1 3.127 0.025 123.031 0 3.077 3.177
22 Fattore_T1 ~1 0.000 0.000 NA NA 0.000 0.000
23 Fattore_T2 ~1 0.000 0.000 NA NA 0.000 0.000
fitMeasures(fit_2, c("cfi", "tli", "rmsea", "srmr")) |> print()
cfi tli rmsea srmr
0.931 0.886 0.187 0.253
Tuttavia, come sottolineato da Little [Lit23], il modello base adeguato richiede l’aggiunta di specifiche aspettative. In particolare, è essenziale presupporre che medie e varianze restino costanti nel tempo. Questo ampliamento del modello nullo offre un punto di confronto idoneo per analizzare e interpretare efficacemente i dati longitudinali.
mod_3 <- "
# Definizione dei fattori latenti al tempo T1
Fattore_T1 =~ NA*PAT1P1 + b1*PAT1P2 + b2*PAT1P3
# Definizione dei fattori latenti al tempo T2
Fattore_T2 =~ NA*PAT2P1 + b1*PAT2P2 + b2*PAT2P3
# Varianza dei fattori latenti
Fattore_T1 ~~ c1*Fattore_T1
Fattore_T2 ~~ c1*Fattore_T2
# Covarianza tra i fattori latenti (assumendo che sia 0)
Fattore_T1 ~~ 0*Fattore_T2
# Definizione degli errori di misurazione per gli indicatori al tempo T1
PAT1P1 ~~ a1*PAT1P1
PAT1P2 ~~ a2*PAT1P2
PAT1P3 ~~ a3*PAT1P3
# Definizione degli errori di misurazione per gli indicatori al tempo T2
PAT2P1 ~~ a1*PAT2P1
PAT2P2 ~~ a2*PAT2P2
PAT2P3 ~~ a3*PAT2P3
# Specifica delle medie degli indicatori (intercette) uguali tra i due tempi
# PAT1P1 ~ m1
# PAT1P2 ~ m2
# PAT1P3 ~ m3
# PAT2P1 ~ m1
# PAT2P2 ~ m2
# PAT2P3 ~ m3
"
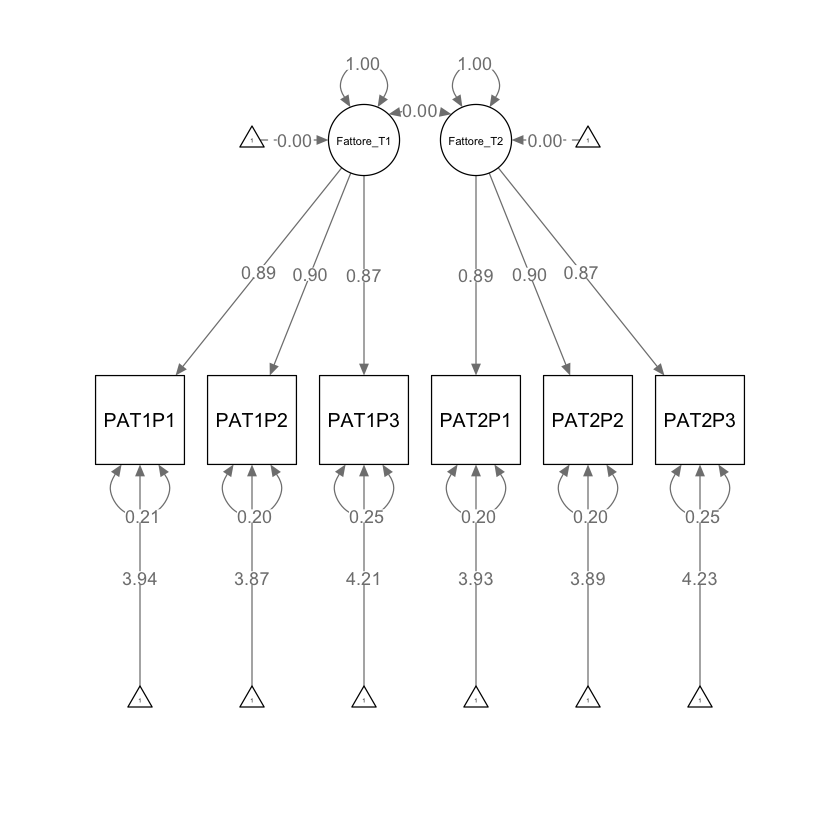
fit_3 <- lavaan::sem(mod_3, data = dat, meanstructure = TRUE)
Warning message in lav_model_vcov(lavmodel = lavmodel, lavsamplestats = lavsamplestats, :
“lavaan WARNING:
The variance-covariance matrix of the estimated parameters (vcov)
does not appear to be positive definite! The smallest eigenvalue
(= 2.757183e-17) is close to zero. This may be a symptom that the
model is not identified.”
semPaths(fit_3,
whatLabels = "std",
sizeMan = 10,
edge.label.cex = 0.9,
style = "mx",
nCharNodes = 0, nCharEdges = 0
)
parameterEstimates(fit_3) |> print()
lhs op rhs label est se z pvalue ci.lower ci.upper
1 Fattore_T1 =~ PAT1P1 0.863 0.018 47.730 0 0.828 0.898
2 Fattore_T1 =~ PAT1P2 b1 0.854 0.012 71.968 0 0.831 0.878
3 Fattore_T1 =~ PAT1P3 b2 0.818 0.012 66.282 0 0.794 0.842
4 Fattore_T2 =~ PAT2P1 0.871 0.018 48.118 0 0.835 0.906
5 Fattore_T2 =~ PAT2P2 b1 0.854 0.012 71.968 0 0.831 0.878
6 Fattore_T2 =~ PAT2P3 b2 0.818 0.012 66.282 0 0.794 0.842
7 Fattore_T1 ~~ Fattore_T1 c1 0.614 0.014 44.667 0 0.587 0.641
8 Fattore_T2 ~~ Fattore_T2 c1 0.614 0.014 44.667 0 0.587 0.641
9 Fattore_T1 ~~ Fattore_T2 0.000 0.000 NA NA 0.000 0.000
10 PAT1P1 ~~ PAT1P1 a1 0.119 0.007 17.380 0 0.105 0.132
11 PAT1P2 ~~ PAT1P2 a2 0.111 0.007 16.933 0 0.098 0.123
12 PAT1P3 ~~ PAT1P3 a3 0.134 0.007 19.941 0 0.121 0.147
13 PAT2P1 ~~ PAT2P1 a1 0.119 0.007 17.380 0 0.105 0.132
14 PAT2P2 ~~ PAT2P2 a2 0.111 0.007 16.933 0 0.098 0.123
15 PAT2P3 ~~ PAT2P3 a3 0.134 0.007 19.941 0 0.121 0.147
16 PAT1P1 ~1 2.992 0.026 113.076 0 2.940 3.044
17 PAT1P2 ~1 2.896 0.026 111.098 0 2.844 2.947
18 PAT1P3 ~1 3.112 0.026 120.907 0 3.062 3.163
19 PAT2P1 ~1 3.002 0.027 112.656 0 2.949 3.054
20 PAT2P2 ~1 2.909 0.026 111.616 0 2.858 2.960
21 PAT2P3 ~1 3.127 0.026 121.471 0 3.076 3.177
22 Fattore_T1 ~1 0.000 0.000 NA NA 0.000 0.000
23 Fattore_T2 ~1 0.000 0.000 NA NA 0.000 0.000
fitMeasures(fit_3, c("cfi", "tli", "rmsea", "srmr")) |> print()
cfi tli rmsea srmr
0.927 0.916 0.160 0.254
Possiamo ora fare il confronto tra il modello di cambiamento latente e l’appropriato modello di confronto.
lavTestLRT(fit_1, fit_3) |> print()
Chi-Squared Difference Test
Df AIC BIC Chisq Chisq diff RMSEA Df diff Pr(>Chisq)
fit_1 5 7427.8 7531.4 6.0645
fit_3 13 7693.5 7759.5 287.8078 281.74 0.20391 8 < 2.2e-16 ***
---
Signif. codes: 0 ‘***’ 0.001 ‘**’ 0.01 ‘*’ 0.05 ‘.’ 0.1 ‘ ’ 1
È evidente che, nel contesto di questi dati, un modello che presuma l’assenza di qualsiasi cambiamento è completamente inadeguato.