85. Modello LCS bivariato#
I modelli LCSM sono stati sviluppati principalmente per studiare le associazioni sequenziali nel tempo tra due o più processi che cambiano nel tempo. In altre parole, le equazioni di cambiamento latente possono essere estese per includere effetti derivanti da variabili aggiuntive per modellare congiuntamente processi multipli di sviluppo in corso (McArdle, 2001; McArdle & Hamagami, 2001). Considereremo qui un modello LCS bivariato con parametri di accoppiamento cambiamento-cambiamento ritardati. Il seguene path diagram è fornito da Wiedemann et al. [WTKovsirE22].
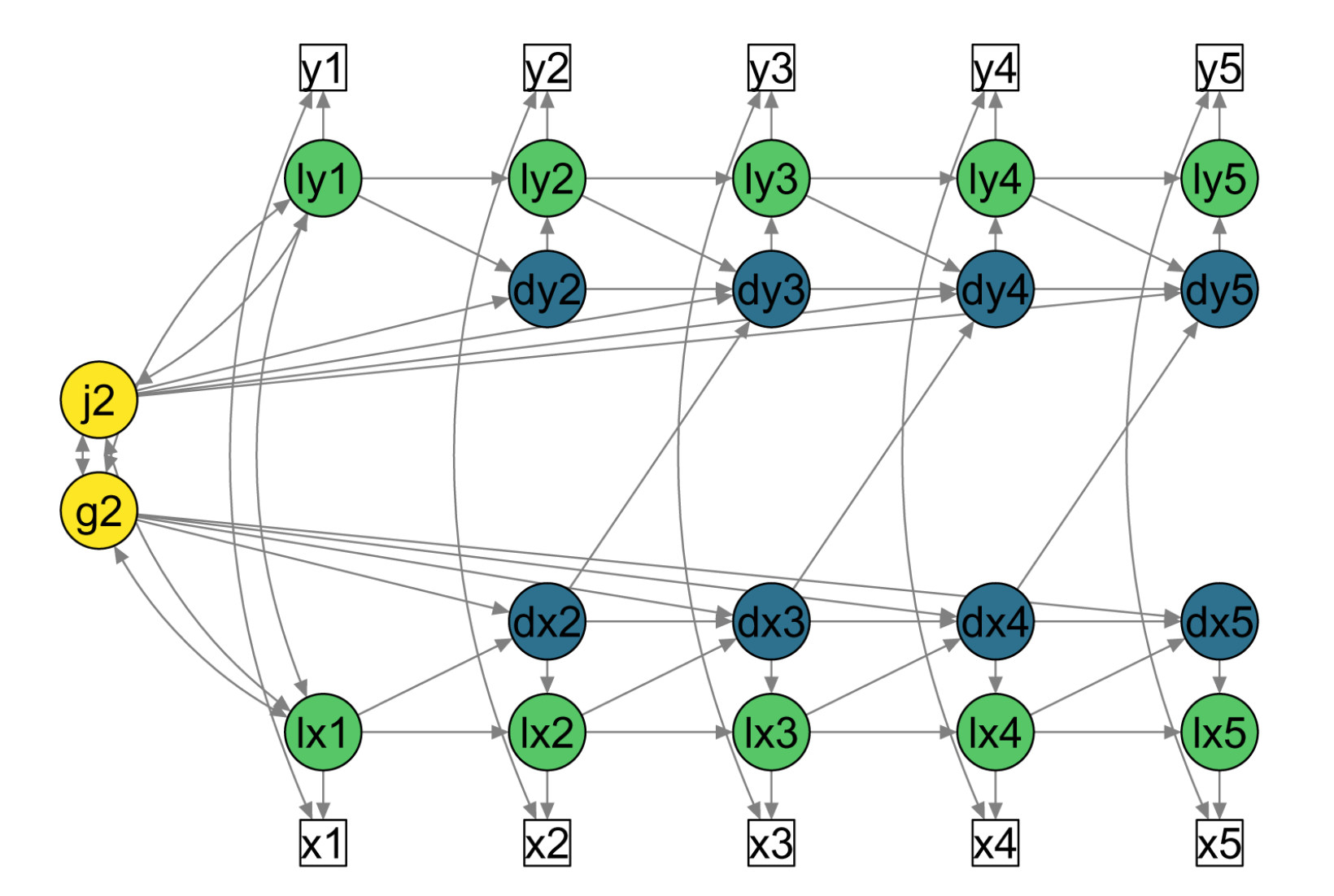
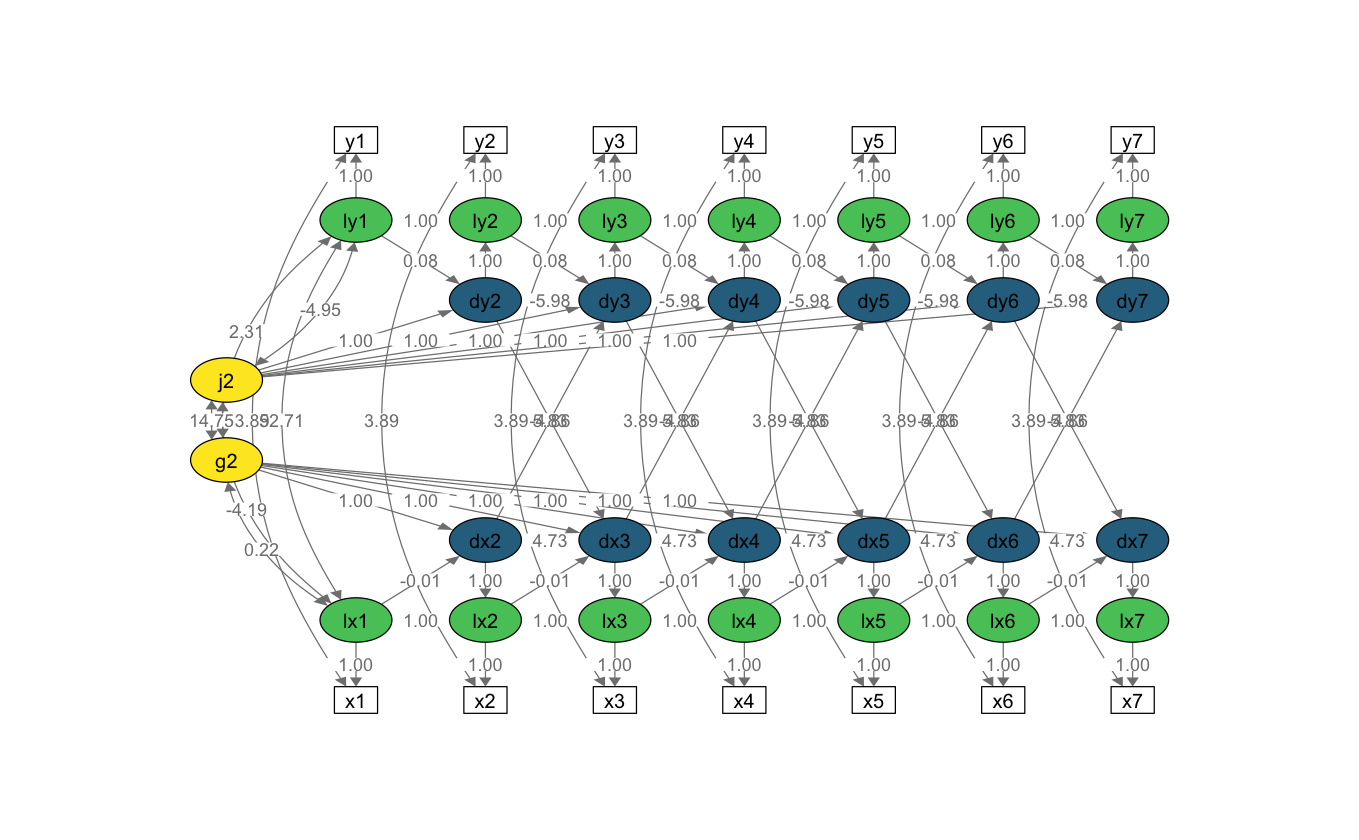
Fig. 85.1 Diagramma di percorso semplificato per un modello LCS bivariato con parametri di accoppiamento cambiamento-cambiamento ritardati (ad esempio, da dx2 a dy3). Quadrati bianchi = variabili osservate; cerchi verdi = punteggi veri latenti (prefisso ‘l’); cerchi blu = punteggi di cambiamento latenti (prefisso ‘d’); cerchi gialli = fattori di cambiamento latente costanti. Frecce direzionali = Regressioni; frecce bidirezionali = covarianze. I punteggi unici (\(ux_t\) e \(uy_t\)) e le varianze uniche (\(σ^2_{ux}\) e \(σ^2_{uy}\)) non sono mostrati in questa figura per semplicità.#
Come in precedenza per il caso del modello univariato, il modello LCSM bivariato include, per ciascuna di due variabili misurate nel tempo, un fattore di cambiamento costante (alpha_constant), un fattore di cambiamento proporzionale (beta) e l’autoregressione dei punteggi di cambiamento (phi). L’aspetto nuovo riguarda i parametri di “accoppiamento”. Per i modelli LCSM bivariati, tali parametri modellano le interazioni tra le variabili \(X\) e \(Y\). I test su tali parametri consentono di affrontare la seguente domanda della ricerca: le variazioni della variabile Y al momento (t) sono determinate dalle variazioni della variabile X al momento precedente (t-1)? E viceversa. Oppure tutte e due le condizioni insieme. I test statistici sui parametri di accoppiamento consentono di rispondere alle domande precedenti.
85.1. Illustrazione#
Per illustrare l’adattamento e l’interpretazione dei modelli LCS bivariati, analizziamo i dati longitudinali di matematica che sono stati utilizzati nel Capitolo 17 di [GRE16]. I dati longitudinali di matematica sono stati raccolti dall’NLSY-CYA (Center for Human Resource Research, 2009) e i punteggi di matematica provengono dal PIAT (Dunn & Markwardt, 1970). Vengono anche misurati i punteggi di comprensione nella lettura dal secondo all’ottavo grado scolastico. Il grado scolastico al momento del test viene utilizzato come metrica temporale e varia dalla seconda elementare (grado 2) alla terza media (grado 8).
Leggiamo i pacchetti necessari.
source("../_common.R")
suppressPackageStartupMessages({
library("lavaan")
library("semPlot")
library("patchwork")
library("psych")
library("DT")
library("kableExtra")
library("lme4")
library("lcsm")
library("tidyr")
library("stringr")
})
set.seed(12345)
Importiamo i dati in R utilizzando un file messo a disposizione dagli autori.
nlsy_multi_data <- read.table(file = "../data/nlsy_math_hyp_wide_R.dat", na.strings = ".")
names(nlsy_multi_data) <- c(
"id", "female", "lb_wght", "anti_k1",
"math2", "math3", "math4", "math5", "math6", "math7", "math8",
"comp2", "comp3", "comp4", "comp5", "comp6", "comp7", "comp8",
"rec2", "rec3", "rec4", "rec5", "rec6", "rec7", "rec8",
"bpi2", "bpi3", "bpi4", "bpi5", "bpi6", "bpi7", "bpi8",
"asl2", "asl3", "asl4", "asl5", "asl6", "asl7", "asl8",
"ax2", "ax3", "ax4", "ax5", "ax6", "ax7", "ax8",
"hds2", "hds3", "hds4", "hds5", "hds6", "hds7", "hds8",
"hyp2", "hyp3", "hyp4", "hyp5", "hyp6", "hyp7", "hyp8",
"dpn2", "dpn3", "dpn4", "dpn5", "dpn6", "dpn7", "dpn8",
"wdn2", "wdn3", "wdn4", "wdn5", "wdn6", "wdn7", "wdn8",
"age2", "age3", "age4", "age5", "age6", "age7", "age8",
"men2", "men3", "men4", "men5", "men6", "men7", "men8",
"spring2", "spring3", "spring4", "spring5", "spring6", "spring7", "spring8",
"anti2", "anti3", "anti4", "anti5", "anti6", "anti7", "anti8"
)
Definiamo due vettori che serviranno per codificare le variabili math e rec.
x_var_list <- paste0("math", 2:8)
y_var_list <- paste0("rec", 2:8)
Estraiamo dal DataFrame originale solo le variabili relative alla matematica e alla capacità di lettura, oltre alla variabile id.
nlsy_multi_data <- nlsy_multi_data[, c("id", x_var_list, y_var_list)]
glimpse(nlsy_multi_data)
Rows: 933
Columns: 15
$ id <int> 201, 303, 2702, 4303, 5002, 5005, 5701, 6102, 6801, 6802, 6803, …
$ math2 <int> NA, 26, 56, NA, NA, 35, NA, NA, NA, NA, NA, 35, NA, NA, NA, NA, …
$ math3 <int> 38, NA, NA, 41, NA, NA, 62, NA, 54, 55, 57, NA, 34, NA, 54, 66, …
$ math4 <int> NA, NA, 58, 58, 46, 50, 61, 55, NA, NA, NA, 59, 50, 48, NA, NA, …
$ math5 <int> 55, 33, NA, NA, NA, NA, NA, 67, 62, 66, 70, NA, NA, NA, NA, 65, …
$ math6 <int> NA, NA, NA, NA, 54, 60, NA, NA, NA, NA, NA, NA, NA, NA, 64, NA, …
$ math7 <int> NA, NA, NA, NA, NA, NA, NA, 81, 66, 68, NA, NA, NA, NA, 63, NA, …
$ math8 <int> NA, NA, 80, NA, 66, 59, NA, NA, NA, NA, NA, NA, NA, NA, NA, NA, …
$ rec2 <int> NA, 26, 33, NA, NA, 47, NA, NA, NA, NA, NA, 33, NA, NA, NA, NA, …
$ rec3 <int> 35, NA, NA, 34, NA, NA, 64, NA, 53, 66, 68, NA, 49, NA, 54, 55, …
$ rec4 <int> NA, NA, 50, 43, 46, 67, 70, 50, NA, NA, NA, 63, 53, 37, NA, NA, …
$ rec5 <int> 52, 35, NA, NA, NA, NA, NA, 69, 76, 66, 70, NA, NA, NA, NA, 78, …
$ rec6 <int> NA, NA, NA, NA, 70, 75, NA, NA, NA, NA, NA, NA, NA, NA, 71, NA, …
$ rec7 <int> NA, NA, NA, NA, NA, NA, NA, 71, 64, 75, NA, NA, NA, NA, 74, NA, …
$ rec8 <int> NA, NA, 66, NA, 77, 78, NA, NA, NA, NA, NA, NA, NA, NA, NA, NA, …
Esaminiamo le statistiche descrittive.
psych::describe(nlsy_multi_data)
| vars | n | mean | sd | median | trimmed | mad | min | max | range | skew | kurtosis | se | |
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| <int> | <dbl> | <dbl> | <dbl> | <dbl> | <dbl> | <dbl> | <dbl> | <dbl> | <dbl> | <dbl> | <dbl> | <dbl> | |
| id | 1 | 933 | 532334.89711 | 3.280208e+05 | 506602.0 | 520130.77108 | 391999.4400 | 201 | 1256601 | 1256400 | 0.28416593 | -0.90788724 | 1.073892e+04 |
| math2 | 2 | 335 | 32.60896 | 1.028600e+01 | 32.0 | 32.27509 | 10.3782 | 12 | 60 | 48 | 0.26866808 | -0.46001296 | 5.619840e-01 |
| math3 | 3 | 431 | 39.88399 | 1.029949e+01 | 41.0 | 39.88406 | 10.3782 | 13 | 67 | 54 | -0.05209289 | -0.32591683 | 4.961091e-01 |
| math4 | 4 | 378 | 46.16931 | 1.016510e+01 | 46.0 | 46.22039 | 8.8956 | 18 | 70 | 52 | -0.05957828 | -0.07596653 | 5.228366e-01 |
| math5 | 5 | 372 | 49.77419 | 9.471909e+00 | 48.0 | 49.76510 | 8.8956 | 23 | 71 | 48 | 0.04254744 | -0.33811258 | 4.910956e-01 |
| math6 | 6 | 390 | 52.72308 | 9.915594e+00 | 50.5 | 52.38462 | 9.6369 | 24 | 78 | 54 | 0.25104168 | -0.38086152 | 5.020956e-01 |
| math7 | 7 | 173 | 55.35260 | 1.062727e+01 | 53.0 | 55.08633 | 11.8608 | 31 | 81 | 50 | 0.21484791 | -0.97096223 | 8.079765e-01 |
| math8 | 8 | 142 | 57.83099 | 1.153101e+01 | 56.0 | 57.42982 | 12.6021 | 26 | 81 | 55 | 0.15905447 | -0.52229674 | 9.676607e-01 |
| rec2 | 9 | 333 | 34.68168 | 1.036303e+01 | 34.0 | 33.89888 | 10.3782 | 15 | 79 | 64 | 0.80847754 | 1.05831429 | 5.678904e-01 |
| rec3 | 10 | 431 | 41.29002 | 1.146468e+01 | 40.0 | 40.80290 | 11.8608 | 19 | 81 | 62 | 0.42959720 | 0.05293611 | 5.522343e-01 |
| rec4 | 11 | 376 | 47.55585 | 1.233346e+01 | 47.0 | 47.16556 | 11.8608 | 21 | 83 | 62 | 0.32275983 | -0.07429087 | 6.360496e-01 |
| rec5 | 12 | 370 | 52.91351 | 1.303500e+01 | 52.0 | 52.86149 | 13.3434 | 21 | 84 | 63 | 0.03724543 | -0.48377604 | 6.776573e-01 |
| rec6 | 13 | 389 | 55.99486 | 1.261831e+01 | 56.0 | 55.92971 | 13.3434 | 21 | 82 | 61 | -0.02930758 | -0.37033988 | 6.397735e-01 |
| rec7 | 14 | 173 | 60.56069 | 1.360801e+01 | 62.0 | 61.15827 | 14.8260 | 23 | 84 | 61 | -0.39192427 | -0.53234704 | 1.034598e+00 |
| rec8 | 15 | 142 | 64.37324 | 1.215246e+01 | 66.0 | 65.10526 | 13.3434 | 32 | 84 | 52 | -0.50329787 | -0.55823690 | 1.019812e+00 |
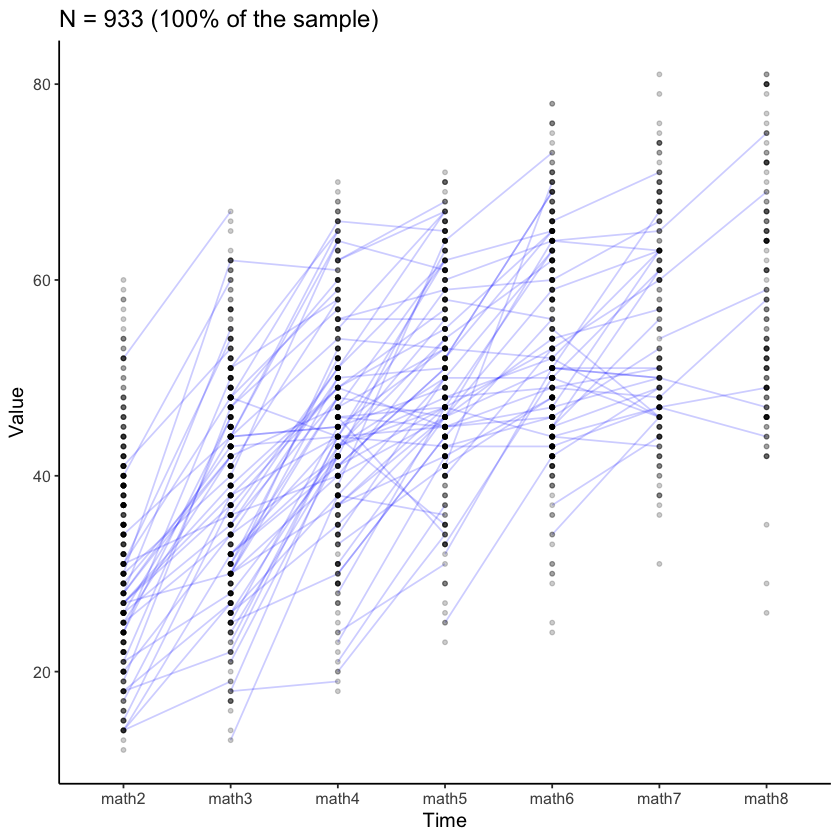
Esaminiamo le traiettorie di crescita nel campione per la matematica.
plot_trajectories(
data = nlsy_multi_data,
id_var = "id",
var_list = x_var_list,
xlab = "Time", ylab = "Value",
connect_missing = FALSE,
# random_sample_frac = 0.018,
title_n = TRUE
)
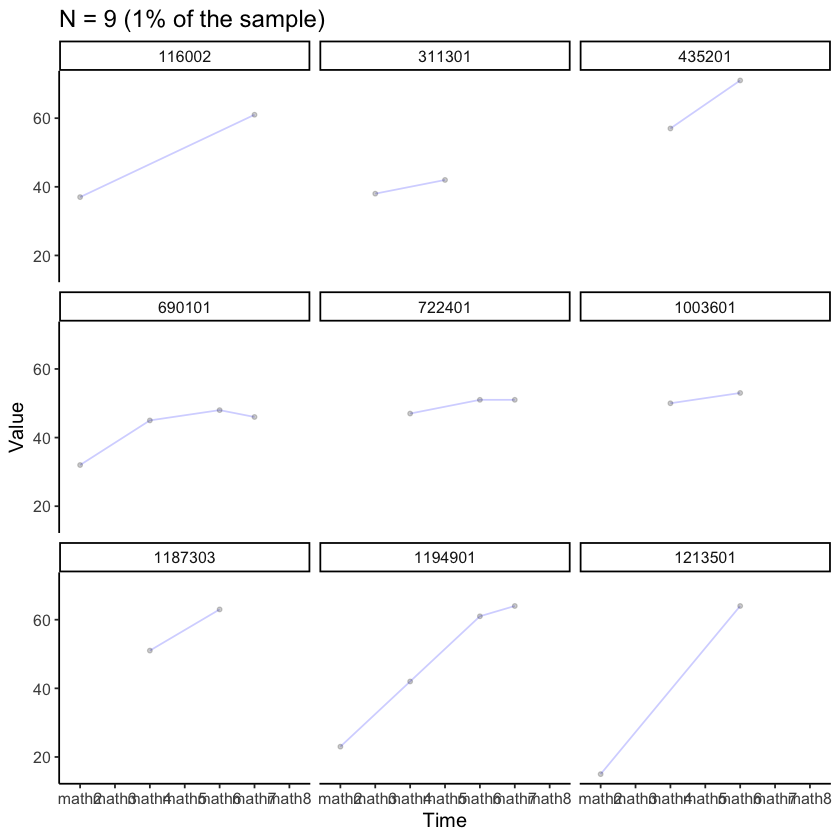
Esaminiamo i dati di alcuni soggetti presi a caso.
plot_trajectories(
data = nlsy_multi_data,
id_var = "id",
var_list = x_var_list,
xlab = "Time", ylab = "Value",
connect_missing = TRUE,
random_sample_frac = 0.01,
title_n = TRUE) +
facet_wrap(~id)
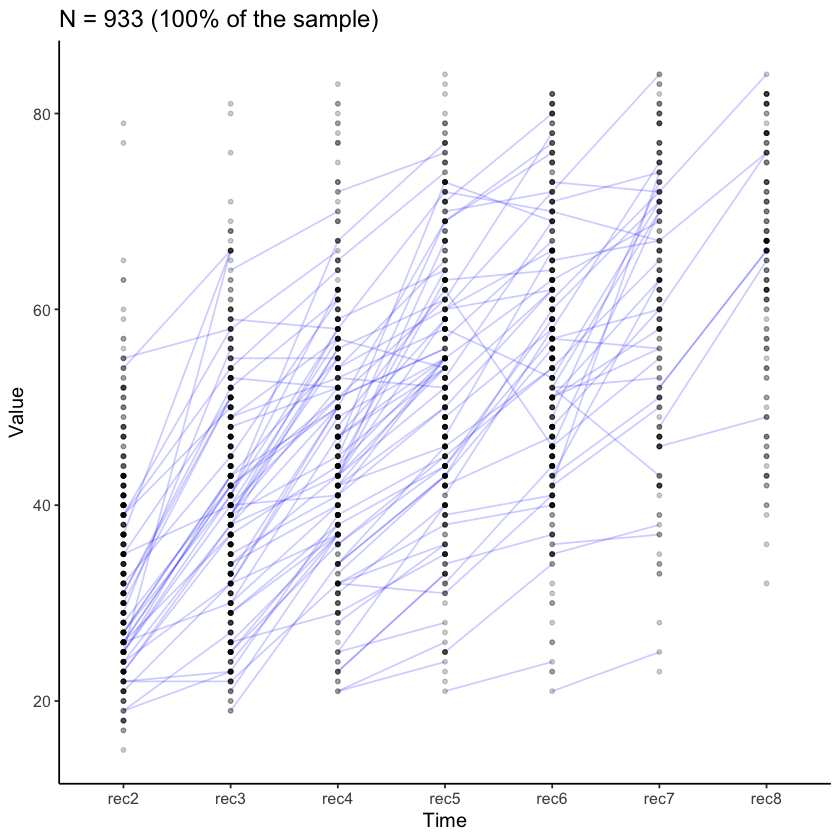
Esaminiamo le curve di crescita per la comprensione nella lettura.
plot_trajectories(
data = nlsy_multi_data,
id_var = "id",
var_list = y_var_list,
xlab = "Time", ylab = "Value",
connect_missing = FALSE,
# random_sample_frac = 0.018,
title_n = TRUE
)
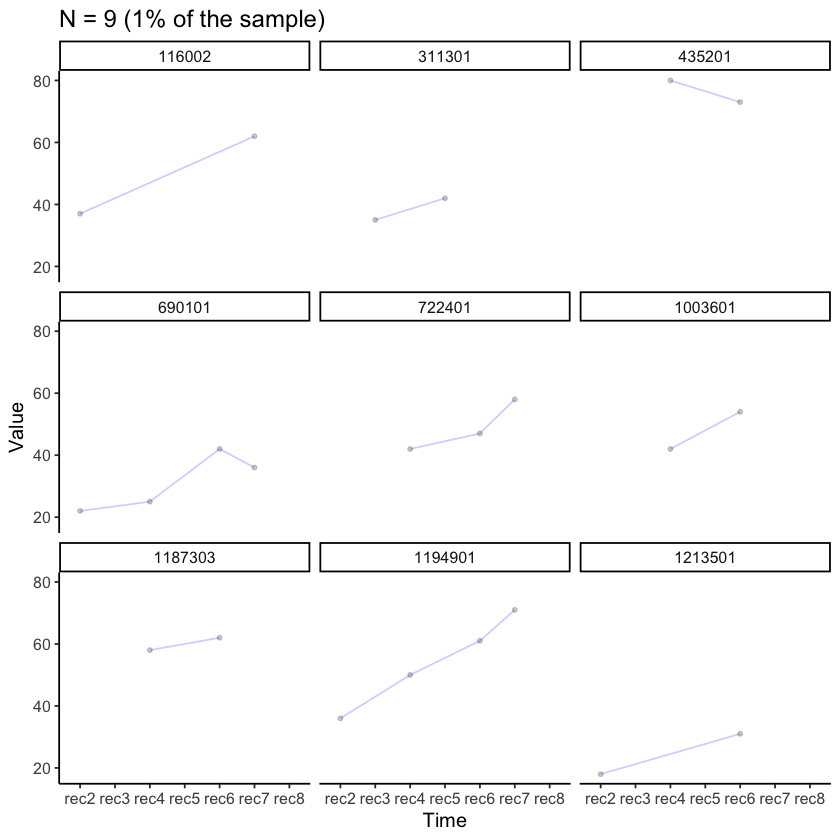
plot_trajectories(
data = nlsy_multi_data,
id_var = "id",
var_list = y_var_list,
xlab = "Time", ylab = "Value",
connect_missing = TRUE,
random_sample_frac = 0.01,
title_n = TRUE) +
facet_wrap(~id)
Adattiamo ora quattro modelli di complessità crescente. Il primo modello ipotizza che i parametri di accoppiamento da matematica a lettura e da lettura a matematica siano pari a zero. È il modello baseline. Il secondo modello ipotizza un effetto da lettura a matematica. Il terzo modello ipotizza un effetto da matematica a lettura. Il quarto modello ipotizza la presenza di entrambi i parametri di accoppiamento.
# baseline: no coupling
multi1_lavaan_results <- fit_bi_lcsm(
data = nlsy_multi_data,
var_x = x_var_list,
var_y = y_var_list,
model_x = list(alpha_constant = TRUE, beta = TRUE, phi = TRUE),
model_y = list(alpha_constant = TRUE, beta = TRUE, phi = TRUE),
coupling = list(xi_lag_xy = FALSE, xi_lag_yx = FALSE)
)
# reading affects change in math
multi2_lavaan_results <- fit_bi_lcsm(
data = nlsy_multi_data,
var_x = x_var_list,
var_y = y_var_list,
model_x = list(alpha_constant = TRUE, beta = TRUE, phi = TRUE),
model_y = list(alpha_constant = TRUE, beta = TRUE, phi = TRUE),
coupling = list(xi_lag_xy = TRUE, xi_lag_yx = FALSE)
)
# math affects change in reading
multi3_lavaan_results <- fit_bi_lcsm(
data = nlsy_multi_data,
var_x = x_var_list,
var_y = y_var_list,
model_x = list(alpha_constant = TRUE, beta = TRUE, phi = TRUE),
model_y = list(alpha_constant = TRUE, beta = TRUE, phi = TRUE),
coupling = list(xi_lag_xy = FALSE, xi_lag_yx = TRUE)
)
# both
multi4_lavaan_results <- fit_bi_lcsm(
data = nlsy_multi_data,
var_x = x_var_list,
var_y = y_var_list,
model_x = list(alpha_constant = TRUE, beta = TRUE, phi = TRUE),
model_y = list(alpha_constant = TRUE, beta = TRUE, phi = TRUE),
coupling = list(xi_lag_xy = TRUE, xi_lag_yx = TRUE)
)
Warning message in lav_data_full(data = data, group = group, cluster = cluster, :
“lavaan WARNING: some cases are empty and will be ignored:
741”
Warning message in lav_data_full(data = data, group = group, cluster = cluster, :
“lavaan WARNING:
due to missing values, some pairwise combinations have less than
10% coverage; use lavInspect(fit, "coverage") to investigate.”
Warning message in lav_mvnorm_missing_h1_estimate_moments(Y = X[[g]], wt = WT[[g]], :
“lavaan WARNING:
Maximum number of iterations reached when computing the sample
moments using EM; use the em.h1.iter.max= argument to increase the
number of iterations”
Warning message in lav_data_full(data = data, group = group, cluster = cluster, :
“lavaan WARNING: some cases are empty and will be ignored:
741”
Warning message in lav_data_full(data = data, group = group, cluster = cluster, :
“lavaan WARNING:
due to missing values, some pairwise combinations have less than
10% coverage; use lavInspect(fit, "coverage") to investigate.”
Warning message in lav_mvnorm_missing_h1_estimate_moments(Y = X[[g]], wt = WT[[g]], :
“lavaan WARNING:
Maximum number of iterations reached when computing the sample
moments using EM; use the em.h1.iter.max= argument to increase the
number of iterations”
È ora possibile fare un confronto tra i vari modelli. Di seguito riportiamo la statistica BIC (valori minori sono preferibili). Dalle statistiche BIC emerge che il modello baseline è da preferire.
c(
extract_fit(multi1_lavaan_results)$bic,
extract_fit(multi2_lavaan_results)$bic,
extract_fit(multi3_lavaan_results)$bic,
extract_fit(multi4_lavaan_results)$bic
) |> print()
[1] 31518.91 31524.44 31526.38 31521.89
Eseguiamo ora i test del rapporto tra verosimiglianze tra i vari modelli.
lavTestLRT(multi1_lavaan_results, multi2_lavaan_results) |>
print()
Scaled Chi-Squared Difference Test (method = "satorra.bentler.2001")
lavaan NOTE:
The "Chisq" column contains standard test statistics, not the
robust test that should be reported per model. A robust difference
test is a function of two standard (not robust) statistics.
Df AIC BIC Chisq Chisq diff Df diff Pr(>Chisq)
multi2_lavaan_results 97 31418 31524 179.14
multi1_lavaan_results 98 31417 31519 180.46 3.4354 1 0.06381 .
---
Signif. codes: 0 '***' 0.001 '**' 0.01 '*' 0.05 '.' 0.1 ' ' 1
lavTestLRT(multi1_lavaan_results, multi3_lavaan_results) |>
print()
Warning message in lavTestLRT(multi1_lavaan_results, multi3_lavaan_results):
"lavaan WARNING:
Some restricted models fit better than less restricted models;
either these models are not nested, or the less restricted model
failed to reach a global optimum. Smallest difference =
-0.633896069371474"
Scaled Chi-Squared Difference Test (method = "satorra.bentler.2001")
lavaan NOTE:
The "Chisq" column contains standard test statistics, not the
robust test that should be reported per model. A robust difference
test is a function of two standard (not robust) statistics.
Df AIC BIC Chisq Chisq diff Df diff Pr(>Chisq)
multi3_lavaan_results 97 31420 31526 181.09
multi1_lavaan_results 98 31417 31519 180.46 -0.17583 1 1
lavTestLRT(multi1_lavaan_results, multi4_lavaan_results) |>
print()
Scaled Chi-Squared Difference Test (method = "satorra.bentler.2001")
lavaan NOTE:
The "Chisq" column contains standard test statistics, not the
robust test that should be reported per model. A robust difference
test is a function of two standard (not robust) statistics.
Df AIC BIC Chisq Chisq diff Df diff Pr(>Chisq)
multi4_lavaan_results 96 31411 31522 169.76
multi1_lavaan_results 98 31417 31519 180.46 5.9923 2 0.04998 *
---
Signif. codes: 0 '***' 0.001 '**' 0.01 '*' 0.05 '.' 0.1 ' ' 1
Anche in questo caso non vi è evidenza che la presenza dei fattori di accoppiamento migliori l’adattamento del modello ai dati.
Per motivi didattici, però, proseguiamo l’analisi ipotizzando una presenza di entrambe le classi di parametri di accoppiamento (da comprensione nella lettura a matematica e viceversa).
multi4_lavaan_syntax <- fit_bi_lcsm(
data = nlsy_multi_data,
var_x = x_var_list,
var_y = y_var_list,
model_x = list(alpha_constant = TRUE, beta = TRUE, phi = TRUE),
model_y = list(alpha_constant = TRUE, beta = TRUE, phi = TRUE),
coupling = list(xi_lag_xy = TRUE, xi_lag_yx = TRUE),
return_lavaan_syntax = TRUE
)
Di seguito riportiamo il path diagram del modello prescelto.
# Plot the results
plot_lcsm(
lavaan_object = multi4_lavaan_results,
lavaan_syntax = multi4_lavaan_syntax,
edge.label.cex = .9,
lcsm_colours = TRUE,
lcsm = "bivariate"
)
Esaminiamo la bontà di adattamento.
extract_fit(multi4_lavaan_results) |> print()
# A tibble: 1 x 8
model chisq npar aic bic cfi rmsea srmr
<chr> <dbl> <dbl> <dbl> <dbl> <dbl> <dbl> <dbl>
1 1 170. 23 31411. 31522. 0.972 0.0287 0.108
Notiamo che le informazioni sull’adattamento del modello fornite da lcsm indicano che il modello di cambiamento duale si adatta bene ai dati con forti indici di adattamento globale (ad esempio, RMSEA inferiore a 0.05, CFI > 0.95).
Esaminiamo i parametri.
extract_param(multi4_lavaan_results) |> print()
# A tibble: 23 x 8
label estimate std.error statistic p.value std.lv std.all std.nox
<chr> <dbl> <dbl> <dbl> <dbl> <dbl> <dbl> <dbl>
1 gamma_lx1 32.5 0.543 60.0 0 4.08 4.08 4.08
2 sigma2_lx1 63.8 4.90 13.0 0 1 1 1
3 sigma2_ux 29.6 1.71 17.3 0 29.6 0.317 0.317
4 alpha_g2 7.82 2.18 3.58 0.000338 2.37 2.37 2.37
5 sigma2_g2 10.9 8.19 1.33 0.183 1 1 1
6 sigma_g2lx1 0.216 6.81 0.0317 0.975 0.00819 0.00819 0.00819
7 beta_x -0.00771 0.0563 -0.137 0.891 -0.0186 -0.0186 -0.0186
8 phi_x 4.73 3.30 1.43 0.152 3.89 3.89 3.89
9 gamma_ly1 33.8 0.422 80.1 0 3.53 3.53 3.53
10 sigma2_ly1 91.5 9.02 10.1 0 1 1 1
# i 13 more rows
L’output completo è fornito qui di seguito.
out = summary(multi4_lavaan_results)
print(out)
lavaan 0.6.17 ended normally after 484 iterations
Estimator ML
Optimization method NLMINB
Number of model parameters 67
Number of equality constraints 44
Used Total
Number of observations 932 933
Number of missing patterns 66
Model Test User Model:
Standard Scaled
Test Statistic 169.764 182.983
Degrees of freedom 96 96
P-value (Chi-square) 0.000 0.000
Scaling correction factor 0.928
Yuan-Bentler correction (Mplus variant)
Parameter Estimates:
Standard errors Sandwich
Information bread Observed
Observed information based on Hessian
Latent Variables:
Estimate Std.Err z-value P(>|z|)
lx1 =~
x1 1.000
lx2 =~
x2 1.000
lx3 =~
x3 1.000
lx4 =~
x4 1.000
lx5 =~
x5 1.000
lx6 =~
x6 1.000
lx7 =~
x7 1.000
dx2 =~
lx2 1.000
dx3 =~
lx3 1.000
dx4 =~
lx4 1.000
dx5 =~
lx5 1.000
dx6 =~
lx6 1.000
dx7 =~
lx7 1.000
g2 =~
dx2 1.000
dx3 1.000
dx4 1.000
dx5 1.000
dx6 1.000
dx7 1.000
ly1 =~
y1 1.000
ly2 =~
y2 1.000
ly3 =~
y3 1.000
ly4 =~
y4 1.000
ly5 =~
y5 1.000
ly6 =~
y6 1.000
ly7 =~
y7 1.000
dy2 =~
ly2 1.000
dy3 =~
ly3 1.000
dy4 =~
ly4 1.000
dy5 =~
ly5 1.000
dy6 =~
ly6 1.000
dy7 =~
ly7 1.000
j2 =~
dy2 1.000
dy3 1.000
dy4 1.000
dy5 1.000
dy6 1.000
dy7 1.000
Regressions:
Estimate Std.Err z-value P(>|z|)
lx2 ~
lx1 1.000
lx3 ~
lx2 1.000
lx4 ~
lx3 1.000
lx5 ~
lx4 1.000
lx6 ~
lx5 1.000
lx7 ~
lx6 1.000
dx2 ~
lx1 (bt_x) -0.008 0.056 -0.137 0.891
dx3 ~
lx2 (bt_x) -0.008 0.056 -0.137 0.891
dx4 ~
lx3 (bt_x) -0.008 0.056 -0.137 0.891
dx5 ~
lx4 (bt_x) -0.008 0.056 -0.137 0.891
dx6 ~
lx5 (bt_x) -0.008 0.056 -0.137 0.891
dx7 ~
lx6 (bt_x) -0.008 0.056 -0.137 0.891
dx3 ~
dx2 (ph_x) 4.731 3.304 1.432 0.152
dx4 ~
dx3 (ph_x) 4.731 3.304 1.432 0.152
dx5 ~
dx4 (ph_x) 4.731 3.304 1.432 0.152
dx6 ~
dx5 (ph_x) 4.731 3.304 1.432 0.152
dx7 ~
dx6 (ph_x) 4.731 3.304 1.432 0.152
ly2 ~
ly1 1.000
ly3 ~
ly2 1.000
ly4 ~
ly3 1.000
ly5 ~
ly4 1.000
ly6 ~
ly5 1.000
ly7 ~
ly6 1.000
dy2 ~
ly1 (bt_y) 0.076 0.041 1.832 0.067
dy3 ~
ly2 (bt_y) 0.076 0.041 1.832 0.067
dy4 ~
ly3 (bt_y) 0.076 0.041 1.832 0.067
dy5 ~
ly4 (bt_y) 0.076 0.041 1.832 0.067
dy6 ~
ly5 (bt_y) 0.076 0.041 1.832 0.067
dy7 ~
ly6 (bt_y) 0.076 0.041 1.832 0.067
dy3 ~
dy2 (ph_y) -5.985 3.231 -1.852 0.064
dy4 ~
dy3 (ph_y) -5.985 3.231 -1.852 0.064
dy5 ~
dy4 (ph_y) -5.985 3.231 -1.852 0.064
dy6 ~
dy5 (ph_y) -5.985 3.231 -1.852 0.064
dy7 ~
dy6 (ph_y) -5.985 3.231 -1.852 0.064
dx3 ~
dy2 (x_lg_x) -4.864 2.915 -1.668 0.095
dx4 ~
dy3 (x_lg_x) -4.864 2.915 -1.668 0.095
dx5 ~
dy4 (x_lg_x) -4.864 2.915 -1.668 0.095
dx6 ~
dy5 (x_lg_x) -4.864 2.915 -1.668 0.095
dx7 ~
dy6 (x_lg_x) -4.864 2.915 -1.668 0.095
dy3 ~
dx2 (x_lg_y) 5.830 3.721 1.566 0.117
dy4 ~
dx3 (x_lg_y) 5.830 3.721 1.566 0.117
dy5 ~
dx4 (x_lg_y) 5.830 3.721 1.566 0.117
dy6 ~
dx5 (x_lg_y) 5.830 3.721 1.566 0.117
dy7 ~
dx6 (x_lg_y) 5.830 3.721 1.566 0.117
Covariances:
Estimate Std.Err z-value P(>|z|)
lx1 ~~
g2 (sgm_g2lx1) 0.216 6.811 0.032 0.975
ly1 ~~
j2 (sgm_j2ly1) -4.945 7.807 -0.633 0.526
.x1 ~~
.y1 (sgm_) 3.888 1.514 2.568 0.010
.x2 ~~
.y2 (sgm_) 3.888 1.514 2.568 0.010
.x3 ~~
.y3 (sgm_) 3.888 1.514 2.568 0.010
.x4 ~~
.y4 (sgm_) 3.888 1.514 2.568 0.010
.x5 ~~
.y5 (sgm_) 3.888 1.514 2.568 0.010
.x6 ~~
.y6 (sgm_) 3.888 1.514 2.568 0.010
.x7 ~~
.y7 (sgm_) 3.888 1.514 2.568 0.010
lx1 ~~
l1 (s_11) 52.706 5.478 9.622 0.000
g2 ~~
l1 (sgm_g2ly1) 2.305 6.817 0.338 0.735
lx1 ~~
j2 (sgm_j2lx1) -4.187 6.344 -0.660 0.509
g2 ~~
j2 (s_22) 14.752 10.409 1.417 0.156
Intercepts:
Estimate Std.Err z-value P(>|z|)
lx1 (gmm_lx1) 32.540 0.543 59.963 0.000
.lx2 0.000
.lx3 0.000
.lx4 0.000
.lx5 0.000
.lx6 0.000
.lx7 0.000
.x1 0.000
.x2 0.000
.x3 0.000
.x4 0.000
.x5 0.000
.x6 0.000
.x7 0.000
.dx2 0.000
.dx3 0.000
.dx4 0.000
.dx5 0.000
.dx6 0.000
.dx7 0.000
g2 (alph_g2) 7.822 2.182 3.584 0.000
ly1 (gmm_ly1) 33.762 0.422 80.067 0.000
.ly2 0.000
.ly3 0.000
.ly4 0.000
.ly5 0.000
.ly6 0.000
.ly7 0.000
.y1 0.000
.y2 0.000
.y3 0.000
.y4 0.000
.y5 0.000
.y6 0.000
.y7 0.000
.dy2 0.000
.dy3 0.000
.dy4 0.000
.dy5 0.000
.dy6 0.000
.dy7 0.000
j2 (alph_j2) 5.289 1.598 3.310 0.001
Variances:
Estimate Std.Err z-value P(>|z|)
lx1 (sgm2_lx1) 63.761 4.904 13.001 0.000
.lx2 0.000
.lx3 0.000
.lx4 0.000
.lx5 0.000
.lx6 0.000
.lx7 0.000
.x1 (sgm2_x) 29.553 1.713 17.251 0.000
.x2 (sgm2_x) 29.553 1.713 17.251 0.000
.x3 (sgm2_x) 29.553 1.713 17.251 0.000
.x4 (sgm2_x) 29.553 1.713 17.251 0.000
.x5 (sgm2_x) 29.553 1.713 17.251 0.000
.x6 (sgm2_x) 29.553 1.713 17.251 0.000
.x7 (sgm2_x) 29.553 1.713 17.251 0.000
.dx2 0.000
.dx3 0.000
.dx4 0.000
.dx5 0.000
.dx6 0.000
.dx7 0.000
g2 (sgm2_g2) 10.913 8.188 1.333 0.183
ly1 (sgm2_ly1) 91.477 9.025 10.136 0.000
.ly2 0.000
.ly3 0.000
.ly4 0.000
.ly5 0.000
.ly6 0.000
.ly7 0.000
.y1 (sgm2_y) 30.320 1.940 15.632 0.000
.y2 (sgm2_y) 30.320 1.940 15.632 0.000
.y3 (sgm2_y) 30.320 1.940 15.632 0.000
.y4 (sgm2_y) 30.320 1.940 15.632 0.000
.y5 (sgm2_y) 30.320 1.940 15.632 0.000
.y6 (sgm2_y) 30.320 1.940 15.632 0.000
.y7 (sgm2_y) 30.320 1.940 15.632 0.000
.dy2 0.000
.dy3 0.000
.dy4 0.000
.dy5 0.000
.dy6 0.000
.dy7 0.000
j2 (sgm2_j2) 20.928 12.318 1.699 0.089
85.1.1. Interpretazione#
Le stime dei parametri di questo modello descrivono le traiettorie medie e individuali per la matematica e la comprensione della lettura, nonché le loro associazioni nel tempo. Le traiettorie medie per la matematica e la comprensione della lettura iniziano rispettivamente a 32.27 e 33.99. Da lì, le traiettorie medie sono descritte dalle rispettive equazioni di cambiamento.
Per l’equazione di cambiamento della matematica, la media della componente di cambiamento costante è 15.82 e indica l’aumento costante ogni anno. La media della componente di cambiamento proporzionale è -0.27, il che indica un effetto limitativo (il coefficiente è negativo) sul cambiamento in matematica dovuto ai punteggi precedenti di matematica. Il modello assume l’assenza di un effetto di accoppiamento (0).
Per l’equazione di cambiamento della comprensione nella lettura, la media della componente di cambiamento costante è 12.59 e indica l’aumento costante ogni anno. La media della componente di cambiamento proporzionale è -0.15, il che indica un effetto limitativo (il coefficiente è negativo) sul cambiamento nella comprensione nella lettura dovuto ai punteggi precedenti di comprensione nella lettura. Il modello assume l’assenza di un effetto di accoppiamento (0).
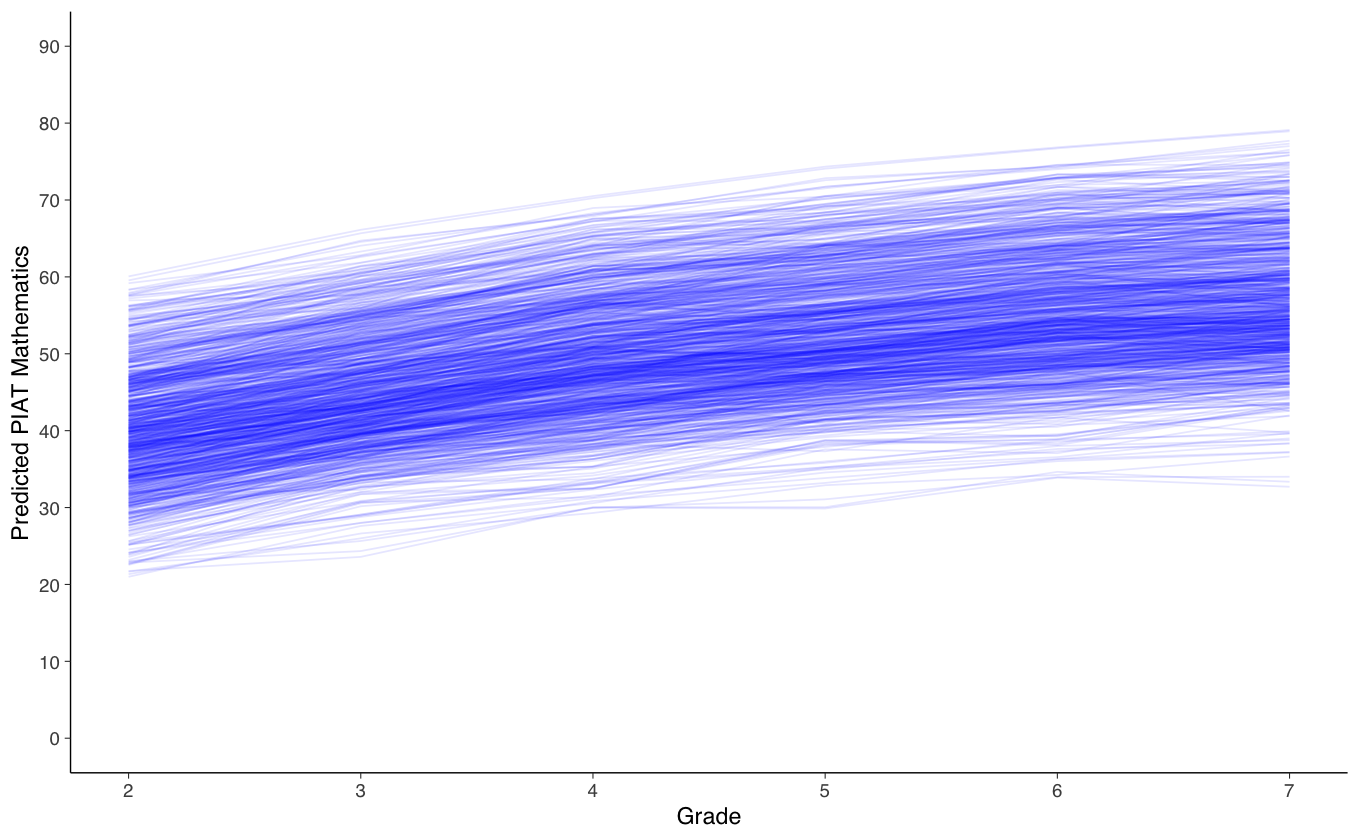
Poniamoci ora il problema di creare una figura che riporta le traiettorie individuali previste dal modello bivariato. Per creare la figura dobbiamo innanzitutto recuperare la sintassi lavaan del modello duale.
Otteniamo i punteggi fattoriali.
nlsy_predicted <- cbind(
nlsy_multi_data$id,
as.data.frame(lavPredict(multi4_lavaan_results, type = "yhat"))
)
names(nlsy_predicted)[1] <- "id"
#looking at data
head(nlsy_predicted)
| id | x1 | x2 | x3 | x4 | x5 | x6 | x7 | y1 | y2 | y3 | y4 | y5 | y6 | y7 | |
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| <int> | <dbl> | <dbl> | <dbl> | <dbl> | <dbl> | <dbl> | <dbl> | <dbl> | <dbl> | <dbl> | <dbl> | <dbl> | <dbl> | <dbl> | |
| 1 | 201 | 33.15176 | 40.43844 | 46.60271 | 50.77319 | 54.73281 | 57.07988 | 59.47240 | 31.45715 | 38.76294 | 45.37727 | 50.08929 | 54.92148 | 58.17234 | 61.73385 |
| 2 | 303 | 24.39926 | 28.98397 | 35.86019 | 37.92657 | 42.93685 | 43.62843 | 47.28636 | 24.58506 | 28.56551 | 35.75247 | 37.65318 | 43.29687 | 44.12950 | 48.64298 |
| 3 | 2702 | 47.54951 | 53.80030 | 60.98284 | 64.20800 | 69.19670 | 70.71387 | 74.12672 | 37.03671 | 42.91439 | 50.50044 | 53.87010 | 59.66067 | 61.68289 | 66.17441 |
| 4 | 4303 | 37.47188 | 42.91769 | 50.78769 | 53.29757 | 58.99872 | 59.89817 | 64.02936 | 31.37796 | 36.16723 | 44.40361 | 46.76698 | 53.21213 | 54.32159 | 59.45710 |
| 5 | 5002 | 33.15122 | 42.56383 | 47.98136 | 53.84208 | 56.81824 | 60.51675 | 61.77965 | 37.95614 | 47.91670 | 53.89218 | 60.88241 | 64.91407 | 70.14310 | 72.81414 |
| 6 | 5005 | 36.26630 | 45.51709 | 49.89202 | 55.82861 | 57.95578 | 61.83941 | 62.39880 | 47.08275 | 57.06728 | 61.98182 | 69.18891 | 72.32670 | 77.84997 | 79.75528 |
Convertiamo i dati in formato long.
predicted_long <- reshape(
data = nlsy_predicted,
varying = c(
"x1", "x2", "x3", "x4", "x5", "x6", "x7",
"y1", "y2", "y3", "y4", "y5", "y6", "y7"
),
timevar = c("grade"),
idvar = c("id"),
direction = "long", sep = ""
)
#sorting for easy viewing
#reorder by id and day
predicted_long <- predicted_long[order(predicted_long$id,predicted_long$grade), ]
#looking at the long data
head(predicted_long, 14)
| id | grade | x | y | |
|---|---|---|---|---|
| <int> | <dbl> | <dbl> | <dbl> | |
| 201.1 | 201 | 1 | 33.15176 | 31.45715 |
| 201.2 | 201 | 2 | 40.43844 | 38.76294 |
| 201.3 | 201 | 3 | 46.60271 | 45.37727 |
| 201.4 | 201 | 4 | 50.77319 | 50.08929 |
| 201.5 | 201 | 5 | 54.73281 | 54.92148 |
| 201.6 | 201 | 6 | 57.07988 | 58.17234 |
| 201.7 | 201 | 7 | 59.47240 | 61.73385 |
| 303.1 | 303 | 1 | 24.39926 | 24.58506 |
| 303.2 | 303 | 2 | 28.98397 | 28.56551 |
| 303.3 | 303 | 3 | 35.86019 | 35.75247 |
| 303.4 | 303 | 4 | 37.92657 | 37.65318 |
| 303.5 | 303 | 5 | 42.93685 | 43.29687 |
| 303.6 | 303 | 6 | 43.62843 | 44.12950 |
| 303.7 | 303 | 7 | 47.28636 | 48.64298 |
Creiamo un grafico del cambiamento intra-individuale per la matematica.
ggplot(data = predicted_long, aes(x = grade, y = x, group = id)) +
#geom_point(color="blue") +
geom_line(color="blue", alpha= 0.1) +
xlab("Grade") +
ylab("Predicted PIAT Mathematics") +
scale_x_continuous(limits=c(2,7), breaks=seq(2,8,by=1)) +
scale_y_continuous(limits=c(0,90), breaks=seq(0,90,by=10))
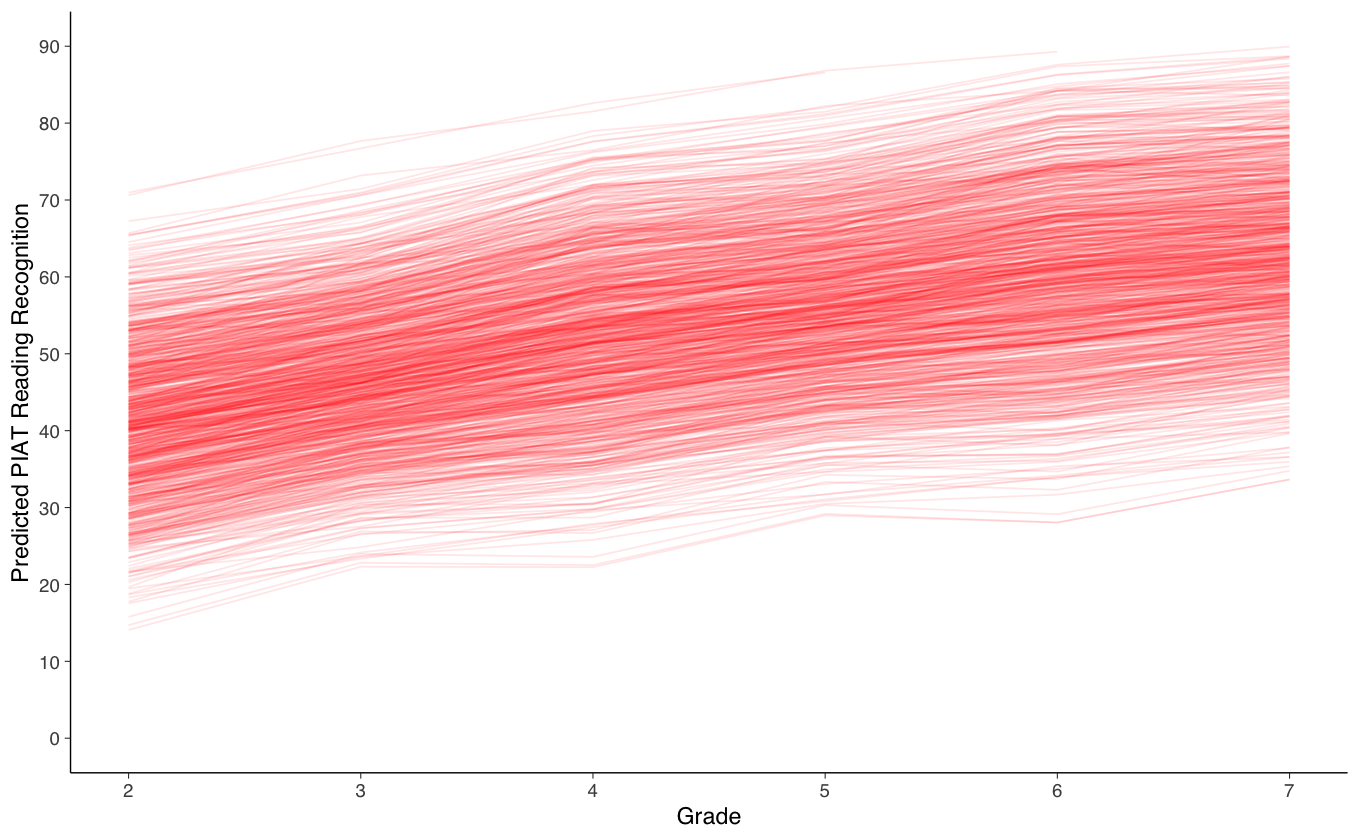
Creiamo un grafico del cambiamento intra-individuale per la comprensione nella lettura.
ggplot(data = predicted_long, aes(x = grade, y = y, group = id)) +
#geom_point(color="red") +
geom_line(color="red", alpha= 0.1) +
xlab("Grade") +
ylab("Predicted PIAT Reading Recognition") +
scale_x_continuous(limits=c(2,7), breaks=seq(2,8,by=1)) +
scale_y_continuous(limits=c(0,90), breaks=seq(0,90,by=10))
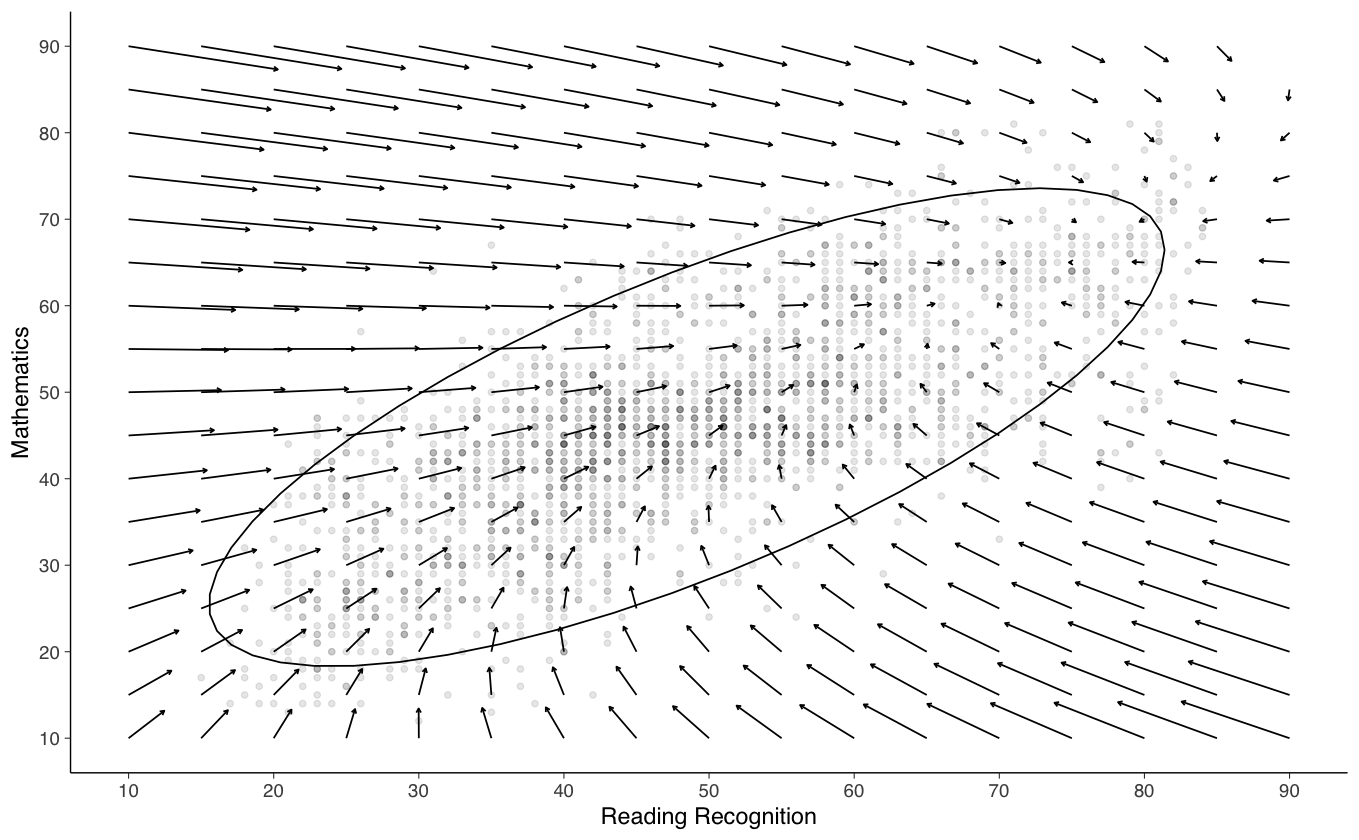
Esaminiamo gli effetti combinati dei cambiamenti nelle due variabili.
# reshaping wide to long
data_long <- reshape(
data = nlsy_multi_data,
varying = c(
"math2", "math3", "math4", "math5", "math6", "math7", "math8",
"rec2", "rec3", "rec4", "rec5", "rec6", "rec7", "rec8"
),
timevar = c("grade"),
idvar = c("id"),
direction = "long", sep = ""
)
#sorting for easy viewing
#reorder by id and day
data_long <- data_long[order(data_long$id,data_long$grade), ]
#looking at the long data
head(data_long, 8)
| id | grade | math | rec | |
|---|---|---|---|---|
| <int> | <dbl> | <int> | <int> | |
| 201.2 | 201 | 2 | NA | NA |
| 201.3 | 201 | 3 | 38 | 35 |
| 201.4 | 201 | 4 | NA | NA |
| 201.5 | 201 | 5 | 55 | 52 |
| 201.6 | 201 | 6 | NA | NA |
| 201.7 | 201 | 7 | NA | NA |
| 201.8 | 201 | 8 | NA | NA |
| 303.2 | 303 | 2 | 26 | 26 |
#creating a grid of starting values
df <- expand.grid(math=seq(10, 90, 5), rec=seq(10, 90, 5))
#calculating change scores for each starting value
#changes in math based on output from model
df$dm <- with(df, 15.09 - 0.293*math + 0.053*rec)
#changes in reading based on output from model
df$dr <- with(df, 10.89 - 0.495*rec + 0.391*math)
#Plotting vector field with .25 unit time change
ggplot(data = df, aes(x = x, y = y)) +
geom_point(data=data_long, aes(x=rec, y=math), alpha=.1) +
stat_ellipse(data=data_long, aes(x=rec, y=math)) +
geom_segment(aes(x = rec, y = math, xend = rec+.25*dr, yend = math+.25*dm), arrow = arrow(length = unit(0.1, "cm"))) +
xlab("Reading Recognition") +
ylab("Mathematics") +
scale_x_continuous(limits=c(10,90), breaks=seq(10,90,by=10)) +
scale_y_continuous(limits=c(10,90), breaks=seq(10,90,by=10))
Il grafico rappresenta l’evoluzione delle variabili nel tempo. Le frecce del campo vettoriale indicano le variazioni previste nello spazio bivariato per un intervallo di tempo di 0.25 unità. Si osserva che i dati si concentrano principalmente all’interno dell’ellisse di confidenza al 95%. Al di fuori di questa area, i vettori direzionali sono interpolati sulla base delle osservazioni e dei modelli derivati dai dati effettivi (cioè all’interno dell’ellisse). Pertanto, è importante evitare di sovrainterpretare le dinamiche al di fuori dell’ellisse.
La regione dello spazio vettoriale in cui i vettori tendono a zero indica le combinazioni di valori delle due variabili per cui non si prevedono ulteriori cambiamenti. L’aspetto più interessante del grafico non è tanto il risultato finale del processo, quanto la descrizione della forza e della direzione del cambiamento per ogni combinazione di valori delle due variabili considerate.